Линейные модели
Сегодня мы познакомимся с линейными моделями. Это простые модели, которые являются частью многих сложных моделей, о которых мы будем рассказывать на нашем курсе.
В основе линейных моделей лежит линейная функция $$\large f(\vec x) = (\vec w, \vec x) +b, $$ где $(\vec w, \vec x)$ — скалярное произведение:
$$\large (\vec w, \vec x) = \sum_{i=1}^n{w_ix_i} = w_1x_1+w_2x_2+...+w_ix_i+ ... + w_nx_n$$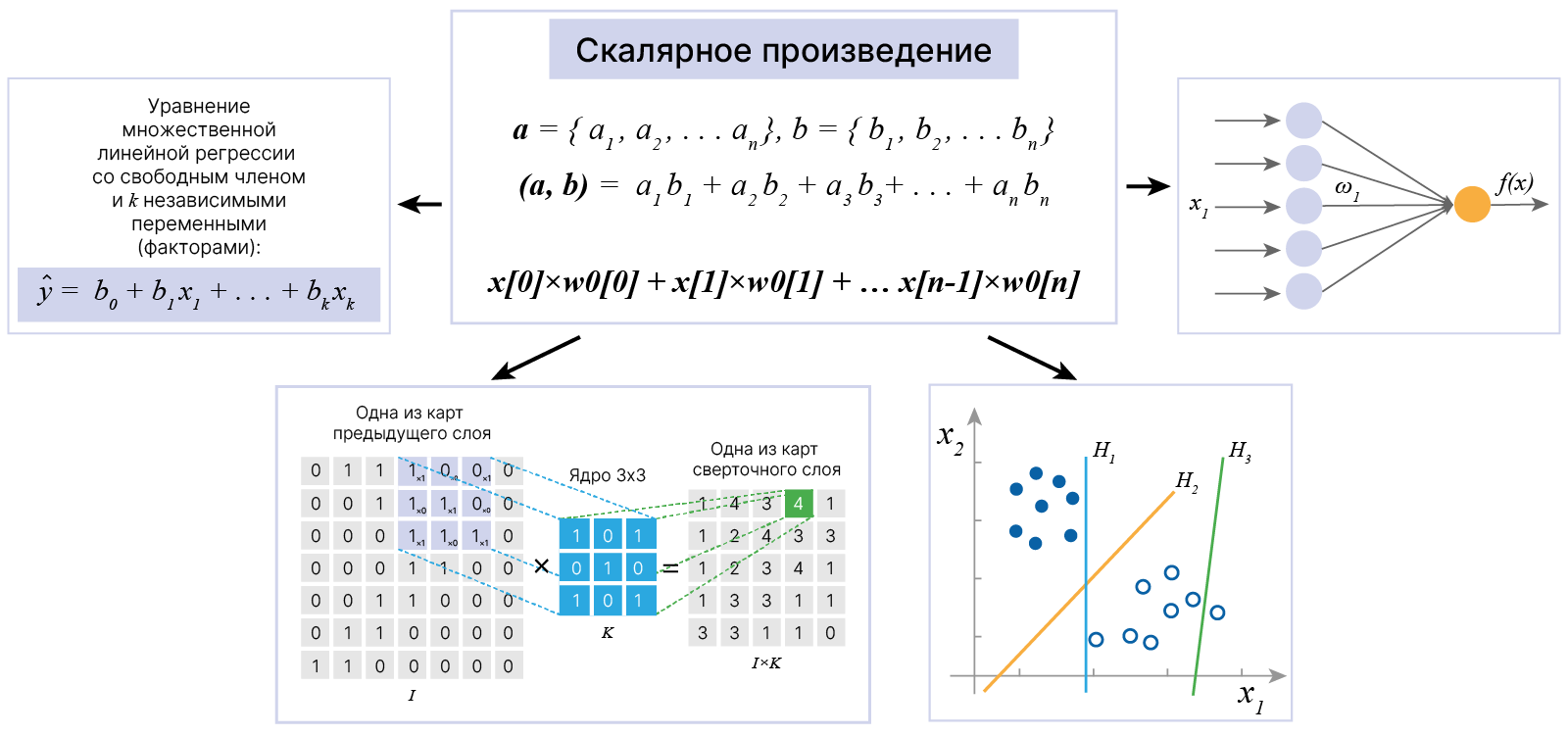
Линейные модели является простыми предшественниками нейронных сетей.
Регрессия — это одна из трех базовых задач машинного обучения (классификация, регрессия, кластеризация).
В задаче регрессии мы используем входные признаки, чтобы предсказать целевые значения. Например, чтобы предсказать цену жилья по его характеристикам (площадь, этаж, год постройки дома, высота потолков, район, ...). Линейная регрессия сводится к тому, чтобы провести “линию наилучшего соответствия” через набор точек данных.
Цель линейной регрессии — поиск линии, которая наилучшим образом соответствует заданным точкам. Напомним, что общее уравнение прямой:
$$\large f(x) = w⋅x + b,$$где $w$ — характеризует наклон линии (в будущем мы будем называть значения $w$ весом, weight) а $b$ — её сдвиг по $y$ (bias). Таким образом, решение линейной регрессии определяет значения для $w$ и $b$ так, что $f (x)$ приближается как можно ближе к $y$. $w$ и $b$ — параметры модели.
Отобразим на графике случайные точки, расположенные в окрестности $y = 3⋅x + 2$
import matplotlib.pyplot as plt
import numpy as np
np.random.seed(0)
x = np.random.rand(100, 1)
y = 2 + 3 * x + (np.random.rand(100, 1) - 0.5)
plt.figure(figsize=(5, 3))
plt.scatter(x, y, s=10)
plt.xlabel("x")
plt.ylabel("y")
plt.show()
Предположим, что нам неизвестны параметры наклона и сдвига $w$ и $b$. Для их определения мы бы могли рассмотреть все возможные прямые вида $f(x) = w⋅x + b$ и выбрать среди семейства прямых такую, которая лучше всего приближает имеющиеся данные:
plt.figure(figsize=(5, 3))
plt.scatter(x, y, s=10)
for w in np.arange(-5.0, 7.0, 1):
for b in [-1, 0, 1, 2, 3]:
y_predicted = b + w * x
plt.plot(x, y_predicted, color="r", alpha=0.3)
plt.xlabel("x")
plt.ylabel("y")
plt.show()
Модель $f(x) = w⋅x + b$ задаёт параметрическое семейство функций, а выбор "правильного" представителя из параметрического семейства и называется обучением модели:
plt.figure(figsize=(5, 3))
plt.scatter(x, y, s=10)
for w in np.arange(-5.0, 7.0, 1):
for b in [-1, 0, 1, 2, 3]:
y_predicted = b + w * x
plt.plot(x, y_predicted, color="r", alpha=0.3)
plt.plot(x, 2 + 3 * x, color="g")
plt.xlabel("x")
plt.ylabel("y")
plt.show()
Как выбрать параметры?
Функция потерь позволяет вычислить меру количества ошибок. Для задачи регрессии такой мерой может быть расстояние между предсказанным значением $f(х)$ и его фактическим значением. Распространенной функцией потерь является средняя квадратичная ошибка (MSE). Чтобы вычислить MSE, мы просто берем все значения ошибок, считаем квадраты их длин и усредняем.
То есть мы определяем ошибку модели на одном объекте как квадрат расстояния между предсказанием и истинным значением, а общая функция потерь будет задана выражением:
$$l_i =|y_i - f(x_i)| $$$$ \text{Loss} = \sum l_i^2 = \frac{1}{N} \sum (y_i - f(x_i))^2$$Для прямой с параметрами $w=4$, $b = 2$ и $w=3$, $b = 2$ (верные значения):
def plot_delta_line(ax, x, y, w, b, color="r"):
y_predicted = w * x + b
# line
ax.plot(x, y_predicted, color=color, alpha=0.5, label=f"f(x)={w}x+{b}")
# delta
for x_i, y_i, f_x in zip(x, y, y_predicted):
ax.vlines(x=x_i, ymin=min(f_x, y_i), ymax=max(f_x, y_i), ls="--", alpha=0.3)
# MSE
loss = np.sum((y - (w * x + b)) ** 2) / (len(x))
ax.set_title(f"MSE = {loss:.3f}")
ax.legend()
fig, axs = plt.subplots(1, 2, figsize=(11, 4))
# plot x_i y_i (dots)
for ax in axs:
ax.scatter(x, y, s=10)
ax.set_xlim([0, 1])
ax.set_ylim([2, 6])
ax.set_xlabel("x")
ax.set_ylabel("y")
plot_delta_line(axs[0], x, y, w=4, b=2, color="r")
plot_delta_line(axs[1], x, y, w=3, b=2, color="g")
plt.show()
Задача поиска оптимальных параметров модели сводится к задаче поиска минимума функции потерь.
Посмотрим, как будет выглядеть ландшафт функции потерь для нашей задачи.
w = np.arange(-10, 30, 1)
b = np.arange(-10, 10, 1)
w, b = np.meshgrid(w, b)
loss = np.zeros_like(w)
for i in range(w.shape[0]):
for j in range(w.shape[1]):
loss[i, j] = np.sum((y - (w[i, j] * x + b[i, j])) ** 2) / (len(x))
fig = plt.figure()
ax = fig.add_subplot(111, projection="3d")
surf = ax.plot_surface(w, b, loss, cmap=plt.cm.RdYlGn_r, alpha=0.5)
ax.contourf(w, b, loss, zdir="z", offset=-1, cmap="RdYlGn_r", alpha=0.5)
ax.set_zlim(0, 20)
ax.set_xlabel("w")
ax.set_ylabel("b")
ax.set_title("MSE")
fig.colorbar(surf, location="left")
plt.show()
Необходимым (но недостаточным) условием локального минимума дифференцируемой функции является равенство нулю частных производных:
$$ \begin{equation*} \begin{cases} \dfrac{\partial \text{Loss}}{\partial w}=0, \\ \dfrac{\partial \text{Loss}}{\partial b}=0. \end{cases} \end{equation*} $$Т.к. MSE для линейной регрессии — полином второй степени относительно $w$ и $b$, а полином второй степени не может иметь больше одного экстремума, то локальный минимум будет глобальным.
Реализуем простейшую модель линейной регрессии с использованием библиотеки NumPy на датасете, определённом выше.
Используем метод наименьших квадратов: МНК, простейшие частные случаи 📚[wiki].
$$w = \frac{n\sum_{i=1}^nx_iy_i - (\sum_{i=1}^nx_i)(\sum_{i=1}^ny_i)}{n\sum_{i=1}^nx_t^2 - (\sum_{i=1}^n x_t)^2};$$$$b = \frac{\sum_{i=1}^ny_i - w(\sum_{i=1}^nx_i)}{n}.$$По сути метод наименьших квадратов — это решение системы уравнений выше.
def estimate_coef(x, y):
n = len(x)
w = (n * sum(np.multiply(x, y)) - sum(x) * sum(y)) / (
n * sum(np.multiply(x, x)) - sum(x) ** 2
)
b = (sum(y) - w * sum(x)) / n
return w, b
w, b = estimate_coef(x, y)
y_predicted = w * x + b
print(f"Estimated coefficients:\nb = {b[0]:.3f} \nw = {w[0]:.3f}")
print(f"Final equation: \ny = {w[0]:.3f}x +{b[0]:.3f}")
plt.figure(figsize=(5, 3))
plt.scatter(x, y, s=10)
plt.plot(x, y_predicted, color="g")
plt.xlabel("x")
plt.ylabel("y")
plt.show()
Estimated coefficients: b = 2.058 w = 2.937 Final equation: y = 2.937x +2.058
Полученное решение близко к исходной зависимости $y=3\cdot x + 2$.
Для многомерного случая МНК можно записать решение 📚[book] в матричном виде:
$$\vec w = (X^TX)^{-1}X^T\vec y$$
где $\vec w$ — вектор параметров модели, включающий $b$ (при записи этого решения используется трюк “столбец единиц”, о котором мы поговорим чуть позже),
$X$ — матрица входных признаков (с единичным столбцом),
$\vec y$ — вектор предсказываемых значений.
С одной из метрик регрессии мы уже познакомились: это $\text{MSE}$, которую мы минимизировали в методе наименьших квадратов. Стоит отметить что $\text{MSE}$ имеет размерность 📚[wiki] квадрата размерности предсказываемого значения.
$$ \text{MSE} = \frac{1}{N} \sum (y_i - f(x_i))^2$$Чтобы получить оценку ошибки той же размерности, можно взять корень (root) от $\text{MSE}$. Это метрика $\text{RMSE}$:
$$ \text{RMSE} = \sqrt{\frac{1}{N} \sum (y_i - f(x_i))^2}$$Или посчитать среднюю абсолютную ошибку $\text{MAE}$:
$$ \text{MAE} = \frac{1}{N} \sum |y_i - f(x_i)|$$Существуют и более специфичные метрики, например $R^2$, которая принимает значения от $(-\inf, 1]$, где $1$ — наилучший вариант. $R^2$ называется коэффициентом детерминации 📚[wiki] и характеризуют долю дисперсии целевого значения, которую объясняет модель.
$$R^2 = 1 - \frac{\text{MSE}}{\sigma^2}=1 - \frac{\sum {(y_i-f(x_i))^2}}{\sum{(y_i-\bar{y})^2}},$$$$\bar{y} = \frac{1}{N}\sum {y_i},$$где $\sigma^2$ — дисперсия.
from sklearn.metrics import mean_squared_error, mean_absolute_error, r2_score
def print_metrics(y_true, y_predicted):
print(f"Mean squared error: {mean_squared_error(y_true, y_predicted):.3f}")
print(
"Root mean squared error: ",
f"{mean_squared_error(y_true, y_predicted, squared=False):.3f}",
)
print(f"Mean absolute error: {mean_absolute_error(y_true, y_predicted):.3f}")
print(f"R2 score: {r2_score(y_true, y_predicted):.3f}")
print_metrics(y, y_predicted)
Mean squared error: 0.076 Root mean squared error: 0.276 Mean absolute error: 0.237 R2 score: 0.904
Подробнее про метрики можно почитать тут 📚[book]. Там же вы можете найти информацию об относительных ошибках, выражаемых в процентах.
Свою линейную регрессию мы написали, теперь изучим, как работать с моделью из Sklearn.
Рассмотрим следующую задачу. Пусть мы хотим построить модель предсказания успеваемости студента на основе информации о величине потраченного им на изучение материала количества времени в часах. Это пример простейшей задачи линейной регрессии.
Загрузим датасет Students Score 🛠️[doc]. Датасет содержит два числовых значения — часы и результаты.
import pandas as pd
dataset = pd.read_csv(
"https://edunet.kea.su/repo/EduNet-web_dependencies/datasets/student_scores.csv"
)
print(dataset.shape)
dataset.head()
(25, 2)
| Hours | Scores | |
|---|---|---|
| 0 | 2.5 | 21 |
| 1 | 5.1 | 47 |
| 2 | 3.2 | 27 |
| 3 | 8.5 | 75 |
| 4 | 3.5 | 30 |
Построим график зависимости одного от другого, а также отобразим распределения каждой из переменных
import seaborn as sns
sns.jointplot(data=dataset, x="Hours", y="Scores", height=5)
plt.show()
Разделим наши данные на train и test
from sklearn.model_selection import train_test_split
x = dataset.iloc[:, :-1].values # column Hours
y = dataset.iloc[:, 1].values # column Score
x_train, x_test, y_train, y_test = train_test_split(
x, y, test_size=0.2, random_state=42
)
В случае сложного, многомодового распределения значений целевой переменной в задаче регрессии, может быть полезно задуматься о стратификации данных. Стратификация данных для задачи регрессии специфична и не реализована в Sklearn, о ней можно почитать в Regression Analysis Based on Stratified Samples 🎓[article], пример кода можно найти на форуме ✏️[blog].
Теперь создадим модель для линейной регрессии. Чтобы не писать с нуля, воспользуемся готовой моделью из библиотеки Sklearn:
from sklearn.linear_model import LinearRegression
regressor = LinearRegression()
И обучим ее
regressor.fit(x_train, y_train)
LinearRegression()In a Jupyter environment, please rerun this cell to show the HTML representation or trust the notebook.
LinearRegression()
Посмотрим, что получилось
x_train.shape
(20, 1)
x_points = np.linspace(min(x_train), max(x_train), 100) # 100 dots at min to max
y_pred = regressor.predict(x_points)
plt.figure(figsize=(6, 4))
plt.plot(x_train, y_train, "o", label="Scores")
plt.plot(
x_points,
y_pred,
label="y = %.2fx+%.2f" % (regressor.coef_[0], regressor.intercept_),
)
plt.title("Hours vs Percentage", size=12)
plt.xlabel("Hours Studied", size=12)
plt.ylabel("Percentage Score", size=12)
plt.legend()
plt.show()
Теперь сделаем предсказание для тестовой выборки
y_pred = regressor.predict(x_test)
x_points = np.linspace(min(x_test), max(x_test), 100)
y_pred = regressor.predict(x_points)
plt.figure(figsize=(6, 4))
plt.plot(x_test, y_test, "o", label="Scores")
plt.plot(
x_points,
y_pred,
label="y = %.2fx+%.2f" % (regressor.coef_[0], regressor.intercept_),
)
plt.title("Hours vs Percentage", size=12)
plt.xlabel("Hours Studied", size=12)
plt.ylabel("Percentage Score", size=12)
plt.legend()
plt.show()
Выглядит неплохо.
Посчитаем метрики для наших значений:
y_pred = regressor.predict(x_test)
print_metrics(y_test, y_pred)
Mean squared error: 18.943 Root mean squared error: 4.352 Mean absolute error: 3.921 R2 score: 0.968
Будьте осторожнее: модели отражают только те закономерности, которые видели в данных. Вероятность того, что студент, потративший на подготовку 20 часов, получит больше максимального балла, мала.
Мы решали задачу линейной регрессии аналитически (МНК), но это не всегда возможно по нескольким причинам:
Давайте поговорим о том, что делать в таком случае.
Метод, который мы будем использовать, называется “метод градиентного спуска”. Для начала вспомним, что такое градиент. Возьмем функцию двух переменных:
$$\large f(x, y) = \sin(x\cdot y)$$Она будет отличаться от функции потерь, которую мы визуализировали, тем, что у нее будет не один экстремум, а сложный рельеф. Рассчитаем ее на диапазоне значений от $0$ до $4$.
import numpy as np
import matplotlib.pyplot as plt
f = lambda x, y: np.sin(x * y)
x = np.linspace(0, 4, 1000)
y = np.linspace(0, 4, 1000)
xx, yy = np.meshgrid(x, y)
zz = f(xx, yy)
fig = plt.figure(figsize=(20, 7))
def show_3d(xx, yy, zz, fig):
ax = fig.add_subplot(121, projection="3d")
surf = ax.plot_surface(xx, yy, zz, cmap=plt.cm.RdYlGn_r)
ax.contourf(xx, yy, zz, zdir="zz", offset=-2, cmap="RdYlGn_r")
ax.set_zlim(-2, 2)
ax.set_xlabel("x")
ax.set_ylabel("y")
ax.set_title("sin(xy)")
fig.colorbar(surf, location="left")
show_3d(xx, yy, zz, fig)
plt.show()
Eсли $\varphi = \varphi(\vec{x})=\varphi(x_1 \dots x_n)$ — функция $n$ переменных, то её градиентом называется $n$-мерный вектор: $$ \nabla \varphi(\vec{x})= \begin{bmatrix} \displaystyle\frac{\partial\varphi}{\partial x_1}\\ \displaystyle\frac{\partial\varphi}{\partial x_2}\\ ...\\ \displaystyle\frac{\partial\varphi}{\partial x_n}\\ \end{bmatrix} $$
Посчитаем градиент нашей функции $f(x, y)$. Для этого воспользуемся таблицей производных 📚[wiki] и правилом вычисления производной сложной функции 📚[wiki] (Chain-rule): $$\frac {\partial f} {\partial x} = \frac {\partial f} {\partial t} \cdot \frac {\partial t} {\partial x}$$
Это правило очень нам пригодится в будущем.
$$\nabla f(x, y)=\begin{bmatrix} \displaystyle\frac{\partial f}{\partial x}\\ \displaystyle\frac{\partial f}{\partial y}\\ \end{bmatrix} =\begin{bmatrix} \displaystyle\frac{\partial\sin(xy)}{\partial(xy)}\cdot\frac{\partial(xy)}{\partial x}\\ \displaystyle\frac{\partial\sin(xy)}{\partial(xy)}\cdot\frac{\partial(xy)}{\partial y}\\ \end{bmatrix} = \begin{bmatrix} \cos(xy)\cdot y\\ \cos(xy)\cdot x\\ \end{bmatrix} $$Посчитаем градиент на том же диапазоне (сетка реже, т.к. мы будем рисовать не точки, а стрелочки):
gradf = lambda x, y: (np.cos(x * y) * y, np.cos(x * y) * x)
xsmall = np.linspace(0, 4, 15)
ysmall = np.linspace(0, 4, 15)
xxsmall, yysmall = np.meshgrid(xsmall, ysmall)
gradx, grady = gradf(xxsmall, yysmall)
Так как значение градиента в точке — это вектор, мы можем говорить о его величине и направлении. Так как значение градиента в точке — это вектор, мы можем говорить о его величине и направлении. Визуализируем наши расчеты: посмотрим на ландшафт функции $f(x, y)$ и направления градиентов.
fig = plt.figure(figsize=(15, 5))
show_3d(xx, yy, zz, fig)
ax = fig.add_subplot(122)
ax.imshow(
zz,
extent=(np.min(x), np.max(x), np.min(y), np.max(y)),
cmap="RdYlGn_r",
origin="lower",
)
ax.set_xlabel("x")
ax.set_ylabel("y")
ax.quiver(xxsmall, yysmall, gradx, grady)
plt.show()
На рисунке выше значения градиента в точке обозначены чёрными стрелочками. Можно заметить, что длина стрелок в районе максимальных и минимальных значений функции почти нулевая, стрелки направлены в направлении возрастания значения функции, и наиболее длинные стрелки находятся в области наиболее резкого изменения значений функции.
Это проявление свойств градиента:
Направление $\dfrac{\nabla f}{||\nabla f||}$ — сообщает нам направление максимального роста функции.
Величина $||\nabla f||$ — характеризует мгновенную скорость изменения значений функции.
Загрузим еще раз данные с зависимостью оценок студентов от времени подготовки.
import pandas as pd
from sklearn.model_selection import train_test_split
dataset = pd.read_csv(
"https://edunet.kea.su/repo/EduNet-web_dependencies/datasets/student_scores.csv"
)
x = dataset.iloc[:, :-1].values # column Hours
y = dataset.iloc[:, 1].values # column Score
x_train, x_test, y_train, y_test = train_test_split(
x, y, test_size=0.2, random_state=42
)
Скачаем код для интерактивной визуализации. Он нужен только для объяснения и не пригодится вам в работе. Его разбирать мы не будем. Eсли интересно, можно изучить самостоятельно.
# @title *Code for interactive visual
# source: https://github.com/TomasBeuzen/deep-learning-with-pytorch
!wget -qN https://edunet.kea.su/repo/EduNet-web_dependencies/dev-2.0/L02/interactive_visualization.py
Для простоты рассмотрим одномерный случай. Будем подбирать только $w$, значение $b$ зафиксируем на уровне $2.83$. Визуализируем ошибку и значения $\dfrac{\partial \text{Loss}}{\partial w}$ для MSE Loss.
from interactive_visualization import plot_grid_search
from sklearn.metrics import mean_squared_error
slopes = np.arange(5, 15, 0.5)
prediction = {f"{w}": w * x_train[:, 0] + 2.83 for w in slopes}
mse = np.array([mean_squared_error(y_train, w * x_train[:, 0] + 2.83) for w in slopes])
dmse_dw = np.array(
[(2 * x_train[:, 0] * (w * x_train[:, 0] + 2.83 - y_train)).mean() for w in slopes]
)
plot_grid_search(x_train[:, 0], y_train, slopes, prediction, mse, dmse_dw)
Видно, что оптимальное значение наклона соответствует минимуму MSE и нулю частной производной $\dfrac{\partial \text{Loss}}{\partial w}$. Аналогично будет, если мы возьмем в качестве Loss MAE.
from sklearn.metrics import mean_absolute_error
slopes = np.arange(5, 15, 0.5)
prediction = {f"{w}": w * x_train[:, 0] + 2.83 for w in slopes}
mae = np.array([mean_absolute_error(y_train, w * x_train[:, 0] + 2.83) for w in slopes])
dmae_dw = np.array(
[
(x_train[:, 0] * np.sign(w * x_train[:, 0] + 2.83 - y_train)).mean()
for w in slopes
]
)
plot_grid_search(x_train[:, 0], y_train, slopes, prediction, mae, dmae_dw)
Итого, т.к. градиент указывает направление наибольшего возрастания функции:
если $\dfrac{\partial \text{Loss}}{\partial w} < 0$, то нам имеет смысл “идти” в сторону возрастания $\displaystyle\frac{\partial \text{Loss}}{\partial w}$;
если $\dfrac{\partial \text{Loss}}{\partial w} > 0$ — в сторону убывания.
Метод градиентного спуска — итеративный метод, идея которого заключается в том, чтобы небольшими шажками “идти” в обратную от градиента сторону:
$$\large \vec w_{n+1} = \vec w_{n} - α \cdot \nabla_{\vec w_{n}} \text{Loss},$$где $α$ — скорость обучения.
Попробуем реализовать это в коде (для простоты только для $w$ при $b=2.83$).
def gradient(x, y, w, b):
return 2 * (x * (w * x + b - y)).mean()
def gradient_descent(x_train, y_train, x_test, y_test, w, alpha, b=2.83, iteration=10):
"""Gradient descent for optimizing slope in simple linear regression"""
# history
ws = [w]
mse_train = [mean_squared_error(y_train, w * x_train + b)]
dmse_train = []
mse_test = [mean_squared_error(y_test, w * x_test + b)]
prediction = {w: w * x_train + b}
print(
f"Iteration 0: w = {w:.2f}, Loss_train = {mse_train[0]:.2f}, "
f"Loss_test = {mse_test[0]:.2f}."
)
for i in range(iteration):
# adjust w based on gradient * learning rate
grad = gradient(x_train, y_train, w, b)
w -= alpha * grad # adjust w based on gradient * learning rate
# history
ws.append(w)
mse_train.append(mean_squared_error(y_train, w * x_train + b))
dmse_train.append(grad)
mse_test.append(mean_squared_error(y_test, w * x_test + b))
prediction[w] = w * x_train + b
print(
f"Iteration {i+1}: w = {w:.2f}, Loss_train = {mse_train[i]:.2f}, "
f"Loss_test = {mse_test[i]:3.2f}."
)
return ws, prediction, mse_train, dmse_train, mse_test
Обучим нашу модель:
slopes, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train[:, 0], y_train, x_test[:, 0], y_test, w=5, alpha=0.01, iteration=7
)
Iteration 0: w = 5.00, Loss_train = 707.84, Loss_test = 793.54. Iteration 1: w = 7.89, Loss_train = 707.84, Loss_test = 793.54. Iteration 2: w = 9.00, Loss_train = 130.56, Loss_test = 145.80. Iteration 3: w = 9.42, Loss_train = 45.98, Loss_test = 42.65. Iteration 4: w = 9.58, Loss_train = 33.58, Loss_test = 24.38. Iteration 5: w = 9.64, Loss_train = 31.77, Loss_test = 20.49. Iteration 6: w = 9.67, Loss_train = 31.50, Loss_test = 19.46. Iteration 7: w = 9.68, Loss_train = 31.46, Loss_test = 19.13.
Визуализируем процесс обучения:
from interactive_visualization import plot_gradient_descent
plot_gradient_descent(x_train[:, 0], y_train, slopes, prediction, mse_train, dmse_train)
Видно, что за $7$ эпох мы получили то же значение $w$, что получали при использовании LinearRegression. При этом мы пришли в минимум $\text{MSE}$ и ноль градиента.
В реальности мы будем работать с функциями многих переменных, поэтому смотреть на сходимость по одной переменной — не самый оптимальный вариант. Более эффективно будет посмотреть на зависимость Loss от количества эпох для train и test.
def plot_mse(mse_train, mse_test):
plt.figure(figsize=(10, 4))
plt.title("Learning curve")
plt.plot(mse_train, label="train")
plt.plot(mse_test, label="test")
plt.legend()
plt.xlabel("iterations", fontsize=12)
plt.ylabel("MSE Loss", fontsize=12)
plt.grid(True)
plt.show()
Такие графики называют кривыми обучения. Посмотрим на кривые обучения при нашей скорости обучения $α=0.01$.
plot_mse(mse_train, mse_test)
Видно, что Loss падает как на train, так и на test выборке. Также мы можем сказать, что сеть обучалась: train и test графики вышли на плато. При этом не произошло переобучение: ошибка на test выборке не начала расти (про переобучение поговорим позже).
В полученных графиках есть особенность, которая бросается в глаза опытному в обучении моделей человеку: Loss на test выборке меньше, чем на train. Это показатель того, что с данными что-то не так. Так бывает при утечке данных (об утечке данных вы подробнее узнаете в следующих лекциях), но в данном случае, test выборка просто слишком мала, чтобы отражать генеральную совокупность (всего 5 студентов, доверительный интервал для такого маленького количества объектов будет широкий).
Скорость (шаг) обучения — некоторый коэффициент, как правило, небольшой, который не позволяет нам двигаться слишком быстро. У нас есть точка, в которую мы хотим попасть. Если мы сделаем слишком большой шаг, то мы ее перескочим (график справа), поэтому надо подобрать шаг, который не позволит ее перескочить, но в то же время такой, чтобы тот же процесс не шел слишком медленно (как на графике слева).

Посмотрим на скорость обучения на нашем примере. При маленькой скорости обучения мы будем очень медленно сходиться к минимуму.
slopes, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train[:, 0], y_train, x_test[:, 0], y_test, w=5, alpha=0.0005, iteration=30
)
Iteration 0: w = 5.00, Loss_train = 707.84, Loss_test = 793.54. Iteration 1: w = 5.14, Loss_train = 707.84, Loss_test = 793.54. Iteration 2: w = 5.28, Loss_train = 666.74, Loss_test = 748.16. Iteration 3: w = 5.42, Loss_train = 628.13, Loss_test = 705.49. Iteration 4: w = 5.55, Loss_train = 591.87, Loss_test = 665.36. Iteration 5: w = 5.68, Loss_train = 557.82, Loss_test = 627.61. Iteration 6: w = 5.80, Loss_train = 525.83, Loss_test = 592.12. Iteration 7: w = 5.92, Loss_train = 495.79, Loss_test = 558.73. Iteration 8: w = 6.04, Loss_train = 467.57, Loss_test = 527.33. Iteration 9: w = 6.15, Loss_train = 441.07, Loss_test = 497.79. Iteration 10: w = 6.26, Loss_train = 416.17, Loss_test = 470.01. Iteration 11: w = 6.37, Loss_train = 392.79, Loss_test = 443.88. Iteration 12: w = 6.47, Loss_train = 370.84, Loss_test = 419.29. Iteration 13: w = 6.57, Loss_train = 350.21, Loss_test = 396.16. Iteration 14: w = 6.66, Loss_train = 330.84, Loss_test = 374.40. Iteration 15: w = 6.76, Loss_train = 312.65, Loss_test = 353.92. Iteration 16: w = 6.85, Loss_train = 295.56, Loss_test = 334.65. Iteration 17: w = 6.93, Loss_train = 279.51, Loss_test = 316.53. Iteration 18: w = 7.02, Loss_train = 264.44, Loss_test = 299.47. Iteration 19: w = 7.10, Loss_train = 250.28, Loss_test = 283.41. Iteration 20: w = 7.18, Loss_train = 236.98, Loss_test = 268.30. Iteration 21: w = 7.26, Loss_train = 224.49, Loss_test = 254.08. Iteration 22: w = 7.33, Loss_train = 212.76, Loss_test = 240.70. Iteration 23: w = 7.41, Loss_train = 201.74, Loss_test = 228.10. Iteration 24: w = 7.48, Loss_train = 191.39, Loss_test = 216.23. Iteration 25: w = 7.54, Loss_train = 181.67, Loss_test = 205.07. Iteration 26: w = 7.61, Loss_train = 172.55, Loss_test = 194.55. Iteration 27: w = 7.67, Loss_train = 163.97, Loss_test = 184.65. Iteration 28: w = 7.74, Loss_train = 155.92, Loss_test = 175.33. Iteration 29: w = 7.80, Loss_train = 148.35, Loss_test = 166.56. Iteration 30: w = 7.85, Loss_train = 141.25, Loss_test = 158.29.
plot_gradient_descent(x_train[:, 0], y_train, slopes, prediction, mse_train, dmse_train)
Спустя 30 итераций оранжевая прямая плохо отражает генеральную совокупность. Мы не достигли минимума MSE и нуля градиента.
Посмотрим, как выглядят кривые обучения:
plot_mse(mse_train, mse_test)
Модель недообучена — значения Loss не вышли на плато.
Посмотрим на достаточно большую скорость обучения.
slopes, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train[:, 0], y_train, x_test[:, 0], y_test, w=5, alpha=0.027, iteration=15
)
Iteration 0: w = 5.00, Loss_train = 707.84, Loss_test = 793.54. Iteration 1: w = 12.80, Loss_train = 707.84, Loss_test = 793.54. Iteration 2: w = 7.60, Loss_train = 331.92, Loss_test = 300.22. Iteration 3: w = 11.07, Loss_train = 164.92, Loss_test = 185.76. Iteration 4: w = 8.76, Loss_train = 90.74, Loss_test = 65.14. Iteration 5: w = 10.30, Loss_train = 57.79, Loss_test = 58.06. Iteration 6: w = 9.27, Loss_train = 43.15, Loss_test = 23.93. Iteration 7: w = 9.96, Loss_train = 36.65, Loss_test = 29.42. Iteration 8: w = 9.50, Loss_train = 33.76, Loss_test = 18.09. Iteration 9: w = 9.80, Loss_train = 32.48, Loss_test = 22.24. Iteration 10: w = 9.60, Loss_train = 31.91, Loss_test = 17.96. Iteration 11: w = 9.74, Loss_train = 31.66, Loss_test = 20.14. Iteration 12: w = 9.65, Loss_train = 31.54, Loss_test = 18.39. Iteration 13: w = 9.71, Loss_train = 31.49, Loss_test = 19.42. Iteration 14: w = 9.67, Loss_train = 31.47, Loss_test = 18.67. Iteration 15: w = 9.69, Loss_train = 31.46, Loss_test = 19.15.
plot_gradient_descent(x_train[:, 0], y_train, slopes, prediction, mse_train, dmse_train)
Шаг, получаемый умножением градиента на скорость обучения, получается достаточно большим, чтобы “перескочить” локальный минимум, но при этом модель все-таки попадает в него. Кривые обучения при этом успешно выходят на плато.
plot_mse(mse_train, mse_test)
В финале посмотрим на очень большую скорость обучения.
slopes, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train[:, 0],
y_train,
x_test[:, 0],
y_test,
w=5,
alpha=0.034,
iteration=5,
)
Iteration 0: w = 5.00, Loss_train = 707.84, Loss_test = 793.54. Iteration 1: w = 14.82, Loss_train = 707.84, Loss_test = 793.54. Iteration 2: w = 4.03, Loss_train = 847.72, Loss_test = 823.37. Iteration 3: w = 15.89, Loss_train = 1016.53, Loss_test = 1132.95. Iteration 4: w = 2.86, Loss_train = 1220.26, Loss_test = 1206.01. Iteration 5: w = 17.17, Loss_train = 1466.11, Loss_test = 1624.33.
Шаг, который мы делаем, слишком большой. Мы не попадаем в локальный минимум.
plot_gradient_descent(x_train[:, 0], y_train, slopes, prediction, mse_train, dmse_train)
По кривым обучения видно, что модель не сошлась: ошибка растет.
plot_mse(mse_train, mse_test)
Выбор скорости обучения будет зависеть от модели и данных. В 7 лекции вы познакомитесь с различными модификациями метода градиентного спуска и узнаете больше о выборе скорости обучения, а пока ориентируйтесь на кривые обучения.
Пока мы настраивали только одну переменную, но даже в случае предсказания оценки по времени подготовки у нас две переменные: вес $w$ и смещение $b$.
Когда признаков станет больше, у нас получится “лапша” из слагаемых: $$y = b + w_1\cdot x_1 + w_2\cdot x_2 + w_3\cdot x_3 + w_4\cdot x_4 + w_5\cdot x_5 + ... + w_n\cdot x_n$$
Нам бы хотелось записать их компактно, чтобы не усложнять код и использовать один и тот же код для данных с разным количеством признаков. Для этого мы будем использовать матричное перемножение и трюк “столбец единиц”, который реализует единый подход к учету смещения.
Обозначим вектор-столбец из настраиваемых параметров: $$\vec w = \begin{bmatrix} b \\ w \\ \end{bmatrix}$$
w = np.array([[0.5], [5]])
w
array([[0.5],
[5. ]])
К матрице (в нашем случае был только один признак, поэтому у нас будет вектор-столбец) признаков слева "дорисуем" столбец единиц: $$X = \begin{bmatrix} 1 & X \\ \end{bmatrix} = \begin{bmatrix} 1 & 2.7 \\ 1 & 3.3 \\ ... & ...\\ 1 & 9.2 \\ \end{bmatrix}$$
Предупреждение: добавлять столбец единиц нужно, только если вы сами пишете модель. Если вы пользуетесь готовыми моделями, в этом нет необходимости.
x_train = np.hstack((np.ones((x_train.shape[0], 1)), x_train))
x_test = np.hstack((np.ones((x_test.shape[0], 1)), x_test))
x_test
array([[1. , 8.3],
[1. , 2.5],
[1. , 2.5],
[1. , 6.9],
[1. , 5.9]])
Матрицу $X$ можно матрично перемножить со столбцом $\vec w$, т.к количество столбцов $X$ совпадает с количеством строк в $\vec w$:
x_train.shape, w.shape
((20, 2), (2, 1))
В общем случае:
$$\large \vec y = b + w_1\cdot x_1 + w_2\cdot x_2 + w_3\cdot x_3 + w_4\cdot x_4 + w_5\cdot x_5 + ... + w_n\cdot x_n = X\vec w $$Эту формулу можно свести к нескольким символам кода (@ — матричное умножение):
y_pred = x_test @ w
y_pred
array([[42.],
[13.],
[13.],
[35.],
[30.]])
Реализуем многомерный градиентный спуск
y_train = np.expand_dims(y_train, axis=1)
y_test = np.expand_dims(y_test, axis=1)
def gradient(x, y, w):
"""Gradient of mean squared error."""
return 2 * (x.T @ (x @ w) - x.T @ y) / len(x)
def gradient_descent(x_train, y_train, x_test, y_test, w, alpha, iteration=10):
"""Gradient descent for optimizing slope in simple linear regression"""
# history
ws = np.zeros((iteration + 1, 2))
ws[0] = w[:, 0]
mse_train = [mean_squared_error(y_train, x_train @ w)]
dmse_train = []
mse_test = [mean_squared_error(y_test, x_test @ w)]
prediction = {(w[0][0], w[1][0]): x_train @ w}
print(
f"Iteration 0: b = {w[0][0]:.2f}, w = {w[1][0]:.2f}, "
f"Loss_train = {mse_train[0]:.2f}, "
f"Loss_test = {mse_test[0]:.2f}."
)
for i in range(iteration):
# adjust w based on gradient * learning rate
grad = gradient(x_train, y_train, w)
w -= alpha * grad # adjust w based on gradient * learning rate
# history
ws[i + 1] = w[:, 0]
mse_train.append(mean_squared_error(y_train, x_train @ w))
dmse_train.append(grad)
mse_test.append(mean_squared_error(y_test, x_test @ w))
prediction[(w[0][0], w[1][0])] = x_train @ w
print(
f"Iteration {i+1}: b = {w[0][0]:.2f}, w = {w[1][0]:.2f}, "
f"Loss_train = {mse_train[i]:.2f}, "
f"Loss_test = {mse_test[i]:3.2f}."
)
return ws, prediction, mse_train, dmse_train, mse_test
Попробуем обучить модель:
w = np.array([[0.5], [5]])
ws, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train,
y_train,
x_test,
y_test,
w,
0.01,
)
Iteration 0: b = 0.50, w = 5.00, Loss_train = 821.48, Loss_test = 915.80. Iteration 1: b = 1.01, w = 8.12, Loss_train = 821.48, Loss_test = 915.80. Iteration 2: b = 1.20, w = 9.26, Loss_train = 138.11, Loss_test = 152.87. Iteration 3: b = 1.28, w = 9.68, Loss_train = 46.20, Loss_test = 41.48. Iteration 4: b = 1.31, w = 9.84, Loss_train = 33.84, Loss_test = 23.27. Iteration 5: b = 1.32, w = 9.89, Loss_train = 32.17, Loss_test = 19.64. Iteration 6: b = 1.33, w = 9.91, Loss_train = 31.95, Loss_test = 18.72. Iteration 7: b = 1.34, w = 9.92, Loss_train = 31.91, Loss_test = 18.44. Iteration 8: b = 1.34, w = 9.92, Loss_train = 31.90, Loss_test = 18.35. Iteration 9: b = 1.35, w = 9.92, Loss_train = 31.90, Loss_test = 18.31. Iteration 10: b = 1.36, w = 9.92, Loss_train = 31.90, Loss_test = 18.30.
Мы не дошли до оптимальной прямой $y = 9.68x+2.83$, которую вычисляли выше.
При этом график Loss выглядит неплохо:
plot_mse(mse_train, mse_test)
Такое поведение связано с ландшафтом функции потерь: значение ошибки по оси $b$ изменяется намного медленнее, чем по оси $w$.
from interactive_visualization import plot_grid_search_2d
intercepts = np.arange(-7.5, 12.5, 0.1) # b
slopes = np.arange(5, 15, 0.1) # w
plot_grid_search_2d(x_train[:, 1], y_train, slopes, intercepts)
Поэтому основное изменение значений происходит вдоль оси $w$, а $b$ меняется слабо (значение $b$ далеко от ожидаемого).
from interactive_visualization import plot_gradient_descent_2d
plot_gradient_descent_2d(
x_train[:, 1],
y_train[:, 0],
ws,
slopes,
intercepts,
)
Чтобы исправить ситуацию, применим StandardScaler:
from sklearn.preprocessing import StandardScaler
scaler = StandardScaler()
x_train_scaled = scaler.fit_transform(np.expand_dims(x_train[:, 1], axis=1)).flatten()
x_test_scaled = scaler.transform(np.expand_dims(x_test[:, 1], axis=1)).flatten()
intercepts = np.arange(40, 60, 0.1) # b
slopes = np.arange(15, 35, 0.1) # w
plot_grid_search_2d(x_train_scaled, y_train, slopes, intercepts)
x_train_scaled = np.hstack(
(np.ones((len(x_train_scaled), 1)), np.expand_dims(x_train_scaled, axis=1)),
)
x_test_scaled = np.hstack(
(np.ones((len(x_test_scaled), 1)), np.expand_dims(x_test_scaled, axis=1)),
)
Т.к. диапазоны x изменились, значения $w$ и $b$ тоже изменятся.
w = np.array([[57.0], [33.0]])
ws, prediction, mse_train, dmse_train, mse_test = gradient_descent(
x_train_scaled, y_train, x_test_scaled, y_test, w, 0.35, iteration=10
)
Iteration 0: b = 57.00, w = 33.00, Loss_train = 146.31, Loss_test = 108.53. Iteration 1: b = 52.70, w = 26.86, Loss_train = 146.31, Loss_test = 108.53. Iteration 2: b = 51.40, w = 25.01, Loss_train = 41.79, Loss_test = 21.10. Iteration 3: b = 51.02, w = 24.46, Loss_train = 32.39, Loss_test = 17.36. Iteration 4: b = 50.90, w = 24.29, Loss_train = 31.54, Loss_test = 18.27. Iteration 5: b = 50.86, w = 24.24, Loss_train = 31.46, Loss_test = 18.72. Iteration 6: b = 50.85, w = 24.23, Loss_train = 31.46, Loss_test = 18.88. Iteration 7: b = 50.85, w = 24.23, Loss_train = 31.45, Loss_test = 18.92. Iteration 8: b = 50.85, w = 24.22, Loss_train = 31.45, Loss_test = 18.94. Iteration 9: b = 50.85, w = 24.22, Loss_train = 31.45, Loss_test = 18.94. Iteration 10: b = 50.85, w = 24.22, Loss_train = 31.45, Loss_test = 18.94.
plot_mse(mse_train, mse_test)
Проверим, что после нормализации мы сходимся к $y = 9.68x + 2.83$. Для этого используем данные о матожидании и дисперсии из StandardScaler.
b = ws[-1][0] - ws[-1][1] * scaler.mean_ / (scaler.var_) ** 0.5
w = ws[-1][1] / (scaler.var_) ** 0.5
print(f"y = {w[0]:.2f}x + {b[0]:.2f}")
y = 9.68x + 2.83
По визуализации видно, что $w$ и $b$ изменяются во время обучения.
plot_gradient_descent_2d(
x_train_scaled[:, 1],
y_train[:, 0],
ws,
slopes,
intercepts,
)
До этого мы обучали модель, рассчитывая градиент по всей train выборке. Это не всегда возможно:
Поэтому появляется идея стохастического градиентного спуска: мы можем делать шаг обучения, рассчитывая градиент не по всей выборке (batch), а по нескольким случайно выбранным объектам (mini-batch) или даже по одному случайно выбранному объекту (stochastic).
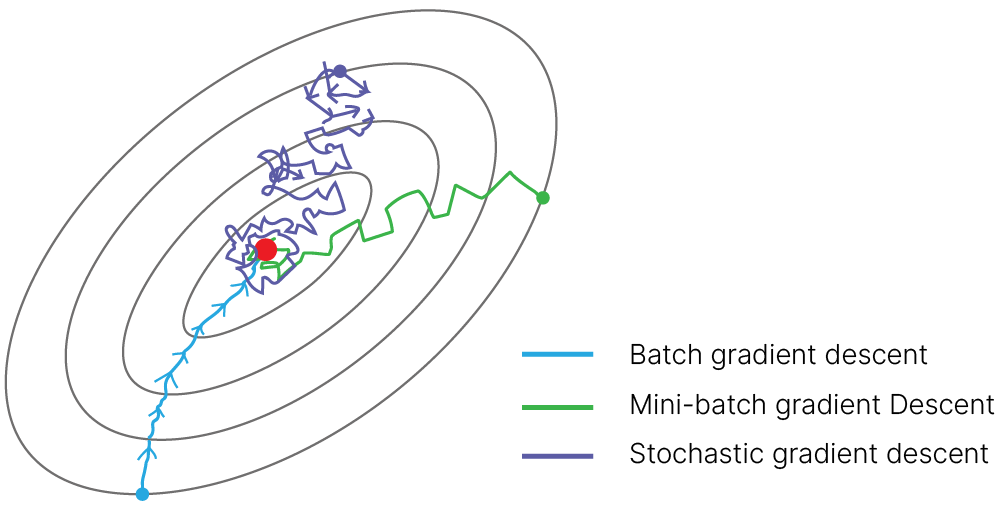
Можно показать 📚[book], что стохастический (с размером $\text{batch}=1$) градиентный спуск сходится к минимуму (глобальному или локальному) функции потерь с конечной точностью. Важным условием является стохастичность. Если мы будем использовать одну и ту же последовательность выборок, это приведет к накоплению ошибки и смещению результата.
Добавим создание подвыборки к нашему алгоритму:
def stochastic_gradient_descent(
x_train,
y_train,
x_test,
y_test,
w,
alpha,
iteration=10,
batch_size=None,
):
"""Gradient descent for optimizing slope in simple linear regression"""
# history
ws = np.zeros((iteration + 1, 2))
ws[0] = w[:, 0]
mse_train = [mean_squared_error(y_train, x_train @ w)]
dmse_train = []
mse_test = [mean_squared_error(y_test, x_test @ w)]
prediction = {(w[0][0], w[1][0]): x_train @ w}
print(
f"Iteration 0: b = {w[0][0]:.2f}, w = {w[1][0]:.2f}, "
f"Loss_train = {mse_train[0]:.2f}, "
f"Loss_test = {mse_test[0]:.2f}."
)
for i in range(iteration):
if not batch_size:
x_sample = x_train
y_sample = y_train
else:
indxs = np.random.choice(x_train.shape[0], batch_size)
x_sample = x_train[indxs, :]
y_sample = y_train[indxs, :]
# adjust w based on gradient * learning rate
grad = gradient(x_sample, y_sample, w)
w -= alpha * grad # adjust w based on gradient * learning rate
# history
ws[i + 1] = w[:, 0]
mse_train.append(mean_squared_error(y_train, x_train @ w))
dmse_train.append(grad)
mse_test.append(mean_squared_error(y_test, x_test @ w))
prediction[(w[0][0], w[1][0])] = x_train @ w
if (i + 1) % 10 == 0:
print(
f"Iteration {i+1}: b = {w[0][0]:.2f}, w = {w[1][0]:.2f}, "
f"Loss_train = {mse_train[i]:.2f}, "
f"Loss_test = {mse_test[i]:3.2f}."
)
return ws, prediction, mse_train, dmse_train, mse_test
Чтобы сравнить результаты, будем использовать одни и те же количество итераций и скорость обучения. Чтобы компенсировать стохастичность, возьмем маленькое значение $\alpha$ и $100$ итераций.
Для всего train сета мы посчитаем градиент для $20\cdot100 = 2000$ точек.
w = np.array([[57.0], [33.0]])
ws, prediction, mse_train, dmse_train, mse_test = stochastic_gradient_descent(
x_train_scaled,
y_train,
x_test_scaled,
y_test,
w,
0.02,
iteration=100,
batch_size=None,
)
f1 = plot_gradient_descent_2d(
x_train_scaled[:, 1],
y_train[:, 0],
ws,
slopes,
intercepts,
mode="lines",
title="Batch gradient descent",
)
Iteration 0: b = 57.00, w = 33.00, Loss_train = 146.31, Loss_test = 108.53. Iteration 10: b = 54.94, w = 30.06, Loss_train = 86.54, Loss_test = 55.92. Iteration 20: b = 53.57, w = 28.10, Loss_train = 55.80, Loss_test = 30.94. Iteration 30: b = 52.66, w = 26.80, Loss_train = 42.22, Loss_test = 21.36. Iteration 40: b = 52.05, w = 25.94, Loss_train = 36.21, Loss_test = 18.09. Iteration 50: b = 51.65, w = 25.36, Loss_train = 33.56, Loss_test = 17.29. Iteration 60: b = 51.38, w = 24.98, Loss_train = 32.38, Loss_test = 17.36. Iteration 70: b = 51.20, w = 24.73, Loss_train = 31.87, Loss_test = 17.68. Iteration 80: b = 51.08, w = 24.56, Loss_train = 31.64, Loss_test = 18.01. Iteration 90: b = 51.01, w = 24.45, Loss_train = 31.54, Loss_test = 18.28. Iteration 100: b = 50.95, w = 24.37, Loss_train = 31.49, Loss_test = 18.49.
Для стохастического градиентного спуска (размер $\text{batch}=1$) мы посчитаем градиент для $1\cdot100 = 100$ точек.
np.random.seed(42)
w = np.array([[57.0], [33.0]])
ws_stohastic, prediction, mse_train, dmse_train, mse_test = stochastic_gradient_descent(
x_train_scaled,
y_train,
x_test_scaled,
y_test,
w,
0.02,
iteration=100,
batch_size=1,
)
f2 = plot_gradient_descent_2d(
x_train_scaled[:, 1],
y_train[:, 0],
ws_stohastic,
slopes,
intercepts,
mode="lines",
title="Stochastic gradient descent",
)
Iteration 0: b = 57.00, w = 33.00, Loss_train = 146.31, Loss_test = 108.53. Iteration 10: b = 54.17, w = 29.83, Loss_train = 74.29, Loss_test = 45.31. Iteration 20: b = 54.43, w = 28.49, Loss_train = 62.91, Loss_test = 37.09. Iteration 30: b = 52.67, w = 26.34, Loss_train = 42.71, Loss_test = 22.04. Iteration 40: b = 51.48, w = 23.96, Loss_train = 32.13, Loss_test = 18.45. Iteration 50: b = 52.13, w = 25.01, Loss_train = 33.79, Loss_test = 17.58. Iteration 60: b = 51.83, w = 25.15, Loss_train = 33.67, Loss_test = 17.93. Iteration 70: b = 52.79, w = 25.67, Loss_train = 37.54, Loss_test = 19.11. Iteration 80: b = 51.72, w = 24.74, Loss_train = 32.47, Loss_test = 17.52. Iteration 90: b = 51.25, w = 25.29, Loss_train = 32.72, Loss_test = 17.30. Iteration 100: b = 50.82, w = 24.18, Loss_train = 31.49, Loss_test = 18.89.
Для стохастического спуска с $\text{mini-batch}=5$ мы посчитаем градиент для $5\cdot100=500$ точек.
np.random.seed(42)
w = np.array([[57.0], [33.0]])
(
ws_mini_batch,
prediction,
mse_train,
dmse_train,
mse_test,
) = stochastic_gradient_descent(
x_train_scaled,
y_train,
x_test_scaled,
y_test,
w,
0.02,
iteration=100,
batch_size=5,
)
f3 = plot_gradient_descent_2d(
x_train_scaled[:, 1],
y_train[:, 0],
ws_mini_batch,
slopes,
intercepts,
mode="lines",
title="Mini-batch gradient descent",
)
Iteration 0: b = 57.00, w = 33.00, Loss_train = 146.31, Loss_test = 108.53. Iteration 10: b = 54.89, w = 29.67, Loss_train = 79.49, Loss_test = 50.29. Iteration 20: b = 53.54, w = 27.93, Loss_train = 52.77, Loss_test = 28.57. Iteration 30: b = 52.28, w = 26.91, Loss_train = 42.28, Loss_test = 21.22. Iteration 40: b = 51.72, w = 25.83, Loss_train = 35.69, Loss_test = 17.80. Iteration 50: b = 51.10, w = 24.92, Loss_train = 32.10, Loss_test = 17.53. Iteration 60: b = 50.84, w = 24.91, Loss_train = 32.06, Loss_test = 17.59. Iteration 70: b = 51.04, w = 24.98, Loss_train = 32.12, Loss_test = 17.46. Iteration 80: b = 51.28, w = 24.72, Loss_train = 31.93, Loss_test = 17.63. Iteration 90: b = 51.03, w = 24.41, Loss_train = 31.56, Loss_test = 18.33. Iteration 100: b = 50.85, w = 23.98, Loss_train = 31.48, Loss_test = 19.36.
Мы ищем минимум для всех данных.
from interactive_visualization import plot_panel
plot_panel(f1, f2, f3)
Для ускорения расчетов рекомендовано использовать максимальный размер mini-batch, который помещается в память, но это не всегда дает лучший результат. На 7 лекции вы увидите, что для сложных моделей стохастичность, связанная с небольшим размером батча, может помочь выбраться из локального минимума и найти более глубокий.
Теперь попробуем разобраться, что делать в случае классификации.
Рассмотрим задачу классификации на два класса. Например, у нас есть данные о лабораторных мышах. Часть из них имеет нормальную массу тела, а часть — мыши с ожирением.

Итак:
В задаче регрессии мы использовали метрику $\text{MSE}$ в качестве функции потерь. Здесь мы можем сделать что-то подобное.
Мы можем ввести пороговое решающее правило: определять метку класса по знаку линейной функции (случай $x = 0$ можем отнести к любому классу):
$$\large y_i^{\text{pred}} = \text{sign}(\vec{w}\vec{x}_i+b)$$где $\text{sign}$ — сигнум-функция (функция знака).
$$\text{sign}(x) = \begin{cases} +1, & x>0, \\ 0 & x=0,\\ -1, & x<0. \end{cases}$$Используя такое решающее правило, мы можем посчитать метрику $\text{accuracy}$:
$$\large \text{accuracy}=\frac{\sum_{i=1}^N [\text{sign}(\vec{w}\vec{x}_i+b)==y_i]}{N}$$Нам нужно максимизировать $\text{accuracy}$, а значит минимизировать $1-\text{accuracy}$. Действуя по аналогии с задачей регрессии, мы могли бы задать функцию потерь следующим образом: $$\large \text{Loss} = 1 - \text{accuracy} = \frac{\sum_{i=1}^N \overline{[\text{sign}(\vec{w}\vec{x}_i+b)==y_i]}}{N} = \frac{\sum_{i=1}^N l_i}{N}$$
$$\large l_i = \overline{[\text{sign}(\vec{w}\vec{x}_i+b)==y_i]}$$Функция $l_i$ будет представлять собой ступеньку (1 — там, где мы ошиблись, и 0 — где класс определен правильно). Это плохо, т.к производная такой функции будет равна нулю почти везде, а это значит, что у нас будут проблемы с поиском минимума.

Мы можем модифицировать функцию потерь, задав оценку сверху для $l_i$, полученного из $accuracy$:
$$\large l_i = \max(0, 1 - y_i ((\vec w, \vec x_i) + b ))$$Данная модификация входит в Hinge loss 📚[wiki]: $$\large \text{Loss} = \frac{1}{2}||w||^2 + C\frac{\sum_{i=1}^N l_i}{N} $$
где $C$ — обратный коэффициент регуляризации, гиперпараметр, значение по умолчанию в Sklearn: C=1.0.
Пока не очень понятно, почему появился член с $w^2$, но он очень важен. Чтобы понять его назначение, рассмотрим задачу геометрически.
Рассмотрим одномерный пример. У нас есть данные только по массе мышей. Часть из них определена как мыши с нормальной массой тела, а часть — как мыши с ожирением.
Чтобы их отделить друг от друга, нам достаточно одного критерия. Мы можем посмотреть на график и визуально определить предельную массу, после которой мыши считаются мышами с ожирением.
import numpy as np
import seaborn as sns
import matplotlib.pyplot as plt
from matplotlib.colors import ListedColormap
custom_cmap = ListedColormap(["#B8E1EC", "#bea6ff", "#FEE7D0"])
def generate_data(total_len=40):
x = np.hstack(
[
np.random.uniform(14, 21, total_len // 2),
np.random.uniform(24, 33, total_len // 2),
]
)
y = np.hstack([np.zeros(total_len // 2), np.ones(total_len // 2)])
return x, y
def plot_data_1d(
x,
y,
total_len=40,
s=50,
threshold=None,
margin=None,
legend=["Normal", "Obese"],
marker="o",
):
ax = sns.scatterplot(x=x, y=np.zeros(len(x)), hue=y, s=s, marker=marker)
if threshold:
x_lim, y_lim = ax.get_xlim(), ax.get_ylim()
XX, YY = np.meshgrid(
np.linspace(x_lim[0], x_lim[1], 100), np.linspace(y_lim[0], y_lim[1], 100)
)
pred = np.sign(XX - threshold)
plt.contourf(XX, YY, pred, alpha=0.3, cmap=custom_cmap)
ax.axvline(threshold, color="grey")
if margin:
for line in margin:
ax.axvline(line, color="grey", ls="dashed")
handles, labels = ax.get_legend_handles_labels()
ax.legend(handles, legend)
ax.set(xlabel="Mass, g")
return ax
total_len = 40
np.random.seed(42)
x, y = generate_data(total_len=total_len)
plt.figure(figsize=(5, 3))
ax = plot_data_1d(x, y, threshold=21.5, total_len=total_len)
Теперь, пользуясь нашим простым критерием, попробуем классифицировать каких-то новых (тестовых) мышей $\color{orange}{✭}$ $\color{blue}{✭}$:
x_test = np.random.uniform(14, 30, 5)
def classify(x, threshold=21.5):
y = np.zeros_like(x)
y[x > threshold] = 1
return y
total_len = 40
threshold = 21.5
plt.figure(figsize=(5, 3))
ax = plot_data_1d(x, y, threshold=threshold, total_len=total_len)
ax = plot_data_1d(
x_test, classify(x_test, threshold), total_len=total_len, s=500, marker="*"
)
Одна из тестовых мышей была классифицирована как мышь с ожирением ($\color{orange}{✭}$ на границе), хотя она ближе по массе к мышам без ожирения из обучающей выборки $\color{blue}{●}$. Не порядок!
Вооружившись этим новым знанием, попробуем классифицировать наших мышек по-умному. Возьмем крайние точки в каждом кластере. И в качестве порогового значения будем использовать среднее между ними.
normal_limit = x[y == 0].max() # extreme point for 'normal'
obese_limit = x[y == 1].min() # extreme point for 'obese'
threshold = np.mean([normal_limit, obese_limit]) # separated with mean value
plt.figure(figsize=(5, 3))
ax = plot_data_1d(
x, y, total_len=total_len, threshold=threshold, margin=[normal_limit, obese_limit]
)
ax = plot_data_1d(
x_test,
classify(x_test, threshold=threshold),
total_len=total_len,
s=500,
marker="*",
)
Мы можем посчитать, насколько наша мышь близка к тому, чтобы оказаться в другом классе. Такое расстояние называется margin. И оно считается как $\mathrm{margin} = |\mathrm{threshold} - \mathrm{observation}|$.
margins = np.abs(x_test - threshold)
print(margins)
[6.65109958 0.68088078 8.053495 5.94541509 4.46323163]
Соответственно, если мы посчитаем margins для наших крайних точек normal_limit и obese_limit, мы найдем самое большое возможное значение margin для нашего классификатора:
margin_0 = np.abs(normal_limit - threshold)
margin_1 = np.abs(obese_limit - threshold)
print(margin_0, margin_1)
1.8143423746730107 1.8143423746730072
Такой классификатор мы называем Maximum Margin Classifier. Он хорошо работает в случае, когда классы не пересекаются.
Теперь рассмотрим пример, где мы измерили не только вес мышей, но и их длину от хвоста до носа. Теперь не очевидно, какие точки кластеров у нас являются крайними и как провести разделяющую прямую, чтобы классы были максимально разнесены.
from sklearn.datasets import make_blobs
def generate_2d_data(total_len=40):
x, y = make_blobs(n_samples=total_len, centers=2, random_state=42)
x[:, 0] += 10
x[:, 1] += 20
return x, y
total_len = 40
x, y = generate_2d_data(total_len=total_len)
fig = plt.figure()
ax = sns.scatterplot(x=x[:, 0], y=x[:, 1], hue=y, s=50)
handles, labels = ax.get_legend_handles_labels()
ax.legend(handles, ["Normal", "Obese"])
ax.set(xlabel="Mass, g", ylabel="Length, cm")
plt.show()
Попробуем подойти к задаче с другой стороны (мы немного упростили визуализацию для удобства восприятия, но с мышками будет так же).
Мы хотим провести разделяющую гиперплоскость таким образом, чтобы:
Второе условие дает нам максимальный зазор (margin), который мы тривиально находили в одномерном случае.
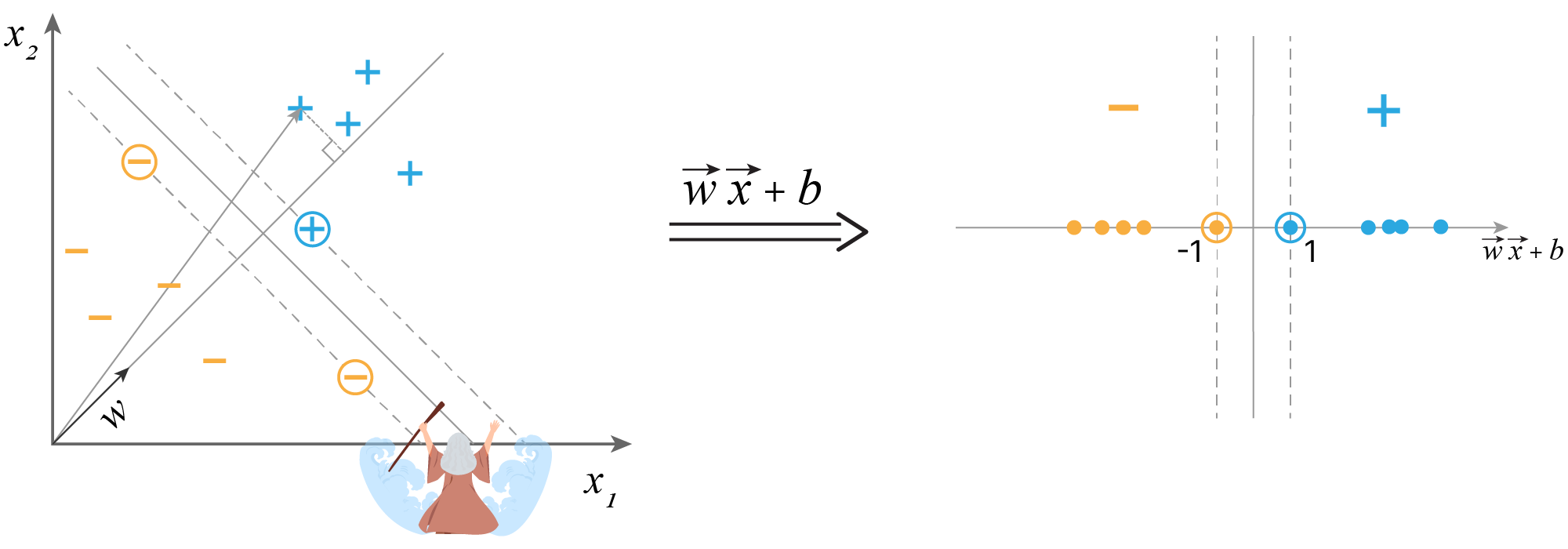
Гиперплоскость однозначно задается вектором нормали $\vec w$ и смещением $b$. Мы ищем решение в виде $(\vec w, \vec x) + b$, где $(\vec w, \vec x)$ — это скалярное произведение, $\vec w$ — вектор весов, а $b$ — смещение. Скалярное произведение вектора признаков на вектор нормали будет давать проекцию вектора признаков на вектор нормали. Мы не будем делать вектор $\vec w$ единичным, вместо этого мы зафиксируем margin на проекции.
Итого:
Метод, использующий проекции опорных векторов для определения разделяющей гиперплоскости, называется SVM (support vector machine).
Условие того, что $i$-й объект лежит по правильную сторону от разделяющих поверхностей, можно записать в совместное условие:
$$\large y_i ((\vec w, \vec x_i) + b )\ge 1,$$которое должно выполняться для всех объектов $1 \le i \le N$.
Среди всех решений $\vec w$ и $b$, которые удовлетворяют условию выше, мы хотим подобрать такое, при котором пороговые разделяющие поверхности будут находится дальше всего. Так как расстояние между ними равно $\displaystyle\frac{2}{||\vec w||}$, мы приходим к следующей задаче на экстремум:
$$\max \frac{2}{||\vec w||} \Leftrightarrow \min \frac{1}{2} ||\vec w||^2$$при условии: $$\large y_i ((\vec w, \vec x_i) + b )\ge 1.$$
Подобная задача на условный экстремум для линейно разделимых классов может быть решена аналитически при помощи метода множителей Лагранжа 📚[wiki]:
Найти $\alpha_i$, $\vec w$ и $b$, которые реализуют минимум функции потерь:
$$\large L = \frac{1}{2} ||\vec w||^2 + \sum_i \alpha_i [y_i ((\vec w, \vec x_i) + b) - 1]$$$\alpha_i\geq0$ — множитель Лагранжа. Он будет не равен нулю только для опорных векторов.
В случае неразделимости классов написанная выше формула переходит в Hinge Loss, $\dfrac{1}{2} ||\vec w||^2$ в котором отвечает за максимальное разнесение классов. SVM c Hinge Loss называют Soft Margin Classifier.
Применим к мышкам метод svm из библиотеки Sklearn.
from sklearn import svm
# Code for illustration, later we will understand how it works
# fit the model, don't regularize for illustration purposes
clf = svm.SVC(kernel="linear", C=1000)
clf.fit(x, y)
fig, axs = plt.subplots(1, 2, figsize=(10, 3))
# first fig
sns.scatterplot(x=x[:, 0], y=x[:, 1], hue=y, s=50, ax=axs[0])
handles, labels = axs[0].get_legend_handles_labels()
axs[0].legend(handles, ["Normal", "Obese"])
axs[0].set(xlabel="Mass, g", ylabel="Length, cm")
# plot the decision function
delta = 0.5
# create grid to evaluate model
YY, XX = np.meshgrid(
np.linspace(x[:, 1].min() - delta, x[:, 1].max() + delta, 30),
np.linspace(x[:, 0].min() - delta, x[:, 0].max() + delta, 30),
)
xy = np.vstack([XX.ravel(), YY.ravel()]).T
Z = clf.decision_function(xy).reshape(XX.shape)
pred = np.sign(Z)
axs[0].contourf(XX, YY, pred, alpha=0.3, cmap=custom_cmap)
# plot decision boget_xlimundary and margins
axs[0].contour(
XX, YY, Z, colors="k", levels=[-1, 0, 1], alpha=0.5, linestyles=["--", "-", "--"]
)
# plot support vectors
axs[0].scatter(
clf.support_vectors_[:, 0],
clf.support_vectors_[:, 1],
s=100,
linewidth=1,
facecolors="none",
edgecolors="k",
)
# second fig
dec_val = clf.decision_function(x)
sns.scatterplot(x=dec_val, y=np.zeros(len(x)), hue=y, ax=axs[1])
x_lim, y_lim = axs[1].get_xlim(), axs[1].get_ylim()
XX, YY = np.meshgrid(
np.linspace(x_lim[0], x_lim[1], 100), np.linspace(y_lim[0], y_lim[1], 100)
)
pred = np.sign(XX)
axs[1].contourf(XX, YY, pred, alpha=0.3, cmap=custom_cmap)
axs[1].axvline(0, color="grey")
axs[1].axvline(-1, color="grey", ls="dashed")
axs[1].axvline(1, color="grey", ls="dashed")
handles, labels = axs[1].get_legend_handles_labels()
axs[1].legend(handles, ["Normal", "Obese"])
axs[1].set(xlabel="wx+b")
sv = clf.decision_function(clf.support_vectors_)
axs[1].scatter(
sv, np.zeros_like(sv), s=100, linewidth=1, facecolors="none", edgecolors="k"
)
plt.show()
Если мы добавим еще одно измерение — возраст, мы обнаружим, что наши данные стали трехмерными, а разделяет их теперь не линия, а плоскость.
def generate_3d_data(total_len=40):
x, y = make_blobs(n_samples=total_len, centers=2, random_state=42, n_features=3)
x[:, 0] += 10
x[:, 1] += 20
x[:, 2] += 10
return x, y
def plot_data(x, y, total_len=40, s=50, threshold=21.5):
fig = plt.figure()
ax = fig.add_subplot(111, projection="3d")
ax.scatter(
xs=x[:, 0], ys=x[:, 1], zs=x[:, 2], c=y, s=s, cmap="tab10", vmin=0, vmax=9
)
# plot the decision function
ax = plt.gca()
xlim = ax.get_xlim()
ylim = ax.get_ylim()
# create grid to evaluate model
xx = np.linspace(xlim[0], xlim[1], 30)
yy = np.linspace(ylim[0], ylim[1], 30)
YY, XX = np.meshgrid(yy, xx)
ax.plot_surface(XX, YY, XX * YY * 0.2, alpha=0.2)
handles, labels = ax.get_legend_handles_labels()
ax.set(xlabel="Mass, g", ylabel="Length, cm", zlabel="Age, days")
return ax
total_len = 40
x, y = generate_3d_data(total_len=total_len)
ax = plot_data(x, y, total_len=total_len)
Соответственно, если бы у нас было 4 измерения и больше (например: вес, длина, возраст, кровяное давление), то многомерная плоскость, которая бы разделяла наши классы, называлась бы гиперплоскость (рисовать мы ее, конечно же, не будем). Чисто технически, и точка, и линия — тоже гиперплоскости. Но все же гиперплоскостью принято называть то, что нельзя нарисовать на бумаге.
Решение задачи SVM, которое мы рассматривали, касалось задачи бинарной классификации. Мы часто будем работать с несколькими классами.
Есть две основные стратегии расширения задачи SVM классификации с двух классов на несколько:
Создадим датасет из 4 классов для демонстрации отличий между этими способами.
centers = [[1, 1], [1, -1], [-1, -1], [-1, 1]]
x, y = make_blobs(n_samples=300, centers=centers, cluster_std=0.50, random_state=42)
dark_colors = ["#1B1464", "#0961A5", "#754C24", "#006837"]
bright_colors = ["#5D5DA6", "#2DA9E1", "#F9B041", "#4AAE4D"]
dull_cmap = ListedColormap(["#D1D5ED", "#B8E1EC", "#FEE7D0", "#C9E3C8"])
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
# first fig
sns.scatterplot(
x=x[:, 0], y=x[:, 1], hue=y, s=50, ax=ax, palette=sns.color_palette(bright_colors)
)
handles, labels = ax.get_legend_handles_labels()
ax.legend(handles, ["0", "1", "2", "3"])
ax.set(xlabel="feature 1", ylabel="feature 2")
plt.xlim([-2.5, 2.5])
plt.ylim([-2.5, 2.5])
plt.show()
Классификация one vs rest реализована в Sklearn в классе svm.LinearSVC:
clf = svm.LinearSVC()
clf.fit(x, y)
LinearSVC()In a Jupyter environment, please rerun this cell to show the HTML representation or trust the notebook.
LinearSVC()
Посмотрим, как выглядят разделяющие прямые и нормали к ним для нашей задачи:
from sklearn.inspection import DecisionBoundaryDisplay
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
disp = DecisionBoundaryDisplay.from_estimator(
clf,
x,
response_method="predict",
cmap=dull_cmap,
alpha=0.8,
xlabel="feature 1",
ylabel="feature 2",
ax=ax,
)
# Plot the training points
sns.scatterplot(
x=x[:, 0], y=x[:, 1], hue=y, s=50, ax=ax, palette=sns.color_palette(bright_colors)
)
# create grid to evaluate model
xx = np.linspace(-2.5, 2.5)
# for visualization
arrow_xs = [0.5, 0.5, -0.5, -0.5]
for i in range(clf.coef_.shape[0]):
coef = clf.coef_[i]
w = -coef[0] / coef[1]
b = -clf.intercept_[0] / coef[1]
yy = w * xx + b
# normal
plt.arrow(
arrow_xs[i],
w * arrow_xs[i] + b,
coef[0] / 4,
coef[1] / 4,
edgecolor=dark_colors[i],
facecolor=bright_colors[i],
width=0.04,
)
# dividing line
plt.plot(xx, yy, dark_colors[i])
plt.xlim([-2.5, 2.5])
plt.ylim([-2.5, 2.5])
plt.show()
Коэффициенты clf.coef_ возвращают вектор нормали. С помощью clf.coef_ и clf.intercept_ можно записать уравнение разделяющей прямой.
Для 4 классов стратегия one vs rest даст 4 разделяющие прямые (гиперплоскости). Количество разделяющих прямых равно количеству классов.
Существует множество модификаций SVM Loss для решения многоклассовой классификации. В литературе вы можете встретить следующую формулировку Loss для SVM задачи:
$$ \text{Loss} = \frac{1}{2} ||\vec w||^2 + {1 \over N}\sum_iL_i(f(x_i,W),y_i),$$$$L_i = \sum_{j\neq y_i}\begin{cases} 0, & \mbox{если } s_{y_i}\geq s_j+1\mbox{} \\ s_j-s_{y_i}+1, & \mbox{если наоборот, то} \mbox{} \end{cases}=\sum_{j\neq y_i}\max(0,s_j-s_{y_i}+1)$$где $s_j = f(x_i, W)_j$ — уравнение для $j$-го класса, $s_{y_i}$ — значение уравнения для истинного класса.
Идея данной формулы аналогична one vs rest, но вместо абсолютных значений используется разница между предсказаниями для различных классов.
Эта формулировка появилась в Support Vector Machines for Multi-Class Pattern Recognition (J. Weston and C. Watkins, 1999) 🎓[article] и стала популярной благодаря Стендфорскому курсу 📚[book], но для нее нет реализации в Sklearn.
Стратегия one vs rest позволяет обучать меньшее количество классификаторов, чем one vs one, но при большом количестве классов могут появляться проблемы, связанные с сильным дисбалансом классов при решении задачи “один против всех”. При большом количестве классов лучше использовать one vs one стратегию.
Второй стратегией многоклассовой классификации для SVM является one vs one, в которой классы разделяются попарно. Эта стратегия реализована в классе svm.SVC.
clf = svm.SVC(kernel="linear")
clf.fit(x, y)
SVC(kernel='linear')In a Jupyter environment, please rerun this cell to show the HTML representation or trust the notebook.
SVC(kernel='linear')
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
disp = DecisionBoundaryDisplay.from_estimator(
clf,
x,
response_method="predict",
cmap=dull_cmap,
alpha=0.8,
xlabel="feature 1",
ylabel="feature 2",
ax=ax,
)
# Plot the training points
sns.scatterplot(
x=x[:, 0], y=x[:, 1], hue=y, s=50, ax=ax, palette=sns.color_palette(bright_colors)
)
# for visualization
arrow_xs = [1, -0.1, 0, -0.17, -0.17, -1]
colors_list = [(0, 1), (0, 2), (0, 3), (1, 2), (1, 3), (2, 3)]
range_list = [(0, 2.5), (-0.3, 0.1), (-0.1, 0.5), (-1, -0.12), (-0.4, 0), (-2.5, 0)]
for i in range(clf.coef_.shape[0]):
xx = np.linspace(*range_list[i])
coef = clf.coef_[i]
w = -coef[0] / coef[1]
b = -clf.intercept_[0] / coef[1]
yy = w * xx + b
# normal
plt.arrow(
arrow_xs[i],
w * arrow_xs[i] + b,
coef[0] / 4,
coef[1] / 4,
edgecolor=dark_colors[colors_list[i][0]],
facecolor=bright_colors[colors_list[i][0]],
width=0.04,
)
# dividing line
plt.plot(xx, yy, dark_colors[colors_list[i][1]])
plt.xlim([-2.5, 2.5])
plt.ylim([-2.5, 2.5])
plt.show()
Для 4 классов стратегия one vs one даст 6 разделяющих прямых (гиперплоскости). Количество разделяющих прямыx: $$ \frac{n_{classes}\cdot (n_{classes}-1)}{2},$$ гдe $n_{classes}$ — количество классов.
Практические советы по использованию SVM:
class_weight и sample_weight (подробнее 🛠️[doc]).Данные не всегда могут быть хорошо разделены (гипер)плоскостью. Например, рассмотрим следующее: у нас есть данные по дозировке лекарства и 2 класса — пациенты, которые поправились, и те, которым лучше не стало.
from matplotlib import pyplot as plt
import seaborn as sns
import numpy as np
def generate_patients_data(total_len=40):
x = np.random.uniform(0, 50, total_len)
y = np.zeros_like(x)
y[(x > 15) & (x < 35)] = 1
return x, y
def plot_data(x, y, total_len=40, s=50):
plt.figure(figsize=(5, 3))
ax = sns.scatterplot(x=x, y=np.zeros(len(x)), hue=y, s=s)
handles, labels = ax.get_legend_handles_labels()
ax.legend(handles, ["Sick", "Recover"])
ax.set(xlabel="dose, mg")
return ax
total_len = 40
x, y = generate_patients_data(total_len=total_len)
ax = plot_data(x, y, total_len=total_len)
plt.show()
Соответственно, мы не можем найти такое пороговое значение, которое будет разделять наши классы на больных и здоровых, а, следовательно, и Support Vector Classifier работать тоже не будет. Для начала давайте преобразуем наши данные таким образом, чтобы они стали 2-хмерными. В качестве значений по оси Y будем использовать дозу, возведенную в квадрат (доза$^2$).
def plot_data(x, y, total_len=40, s=50):
plt.figure(figsize=(5, 3))
ax = sns.scatterplot(x=x[0, :], y=x[1, :], hue=y, s=s)
handles, labels = ax.get_legend_handles_labels()
ax.legend(handles, ["Sick", "Recover"])
ax.set(xlabel="Dose, mg")
ax.set(ylabel="Dose$^2$")
return ax
total_len = 40
x_1, y = generate_patients_data(total_len=total_len)
x_2 = x_1**2
x = np.vstack([x_1, x_2])
plot_data(x, y, total_len=40, s=50)
plt.show()
Теперь мы можем вновь использовать Support Vector Classifier для классификации.
plot_data(x, y, total_len=40, s=50)
x_arr = np.linspace(0, 50, 50)
xs = [x[0, :][y == 1].min(), x[0, :][y == 1].max()]
ys = [x[1, :][y == 1].min(), x[1, :][y == 1].max()]
# Calculate the coefficients.
coefficients = np.polyfit(xs, ys, 1)
# Let's compute the values of the line...
polynomial = np.poly1d(coefficients)
y_axis = polynomial(x_arr)
# ...and plot the points and the line
plt.plot(x_arr, y_axis, "r--")
plt.show()
Основная идея Kernel SVM состоит в том, что мы можем перейти в пространство большей размерности, в котором данные будут линейно разделимы.
Но тут возникает резонный вопрос: почему мы решили возвести в квадрат? Почему не в куб? Или, наоборот, не извлечь корень? Как нам решить, какое преобразование использовать?
И у нас есть вторая проблема — а если перейти надо в пространство очень большой размерности? В этом случае наши данные очень сильно увеличатся в размере.
Комбинация двух проблем дает нам много сложности: надо перебирать большое число возможных пространств большей размерности.
Однако основная фишка Support Vector Machine состоит в том, что внутри он работает на скалярных произведениях. И можно эти скалярные произведения считать, не переходя в пространство большей размерности.
Для этого SVM использует Kernel Function.
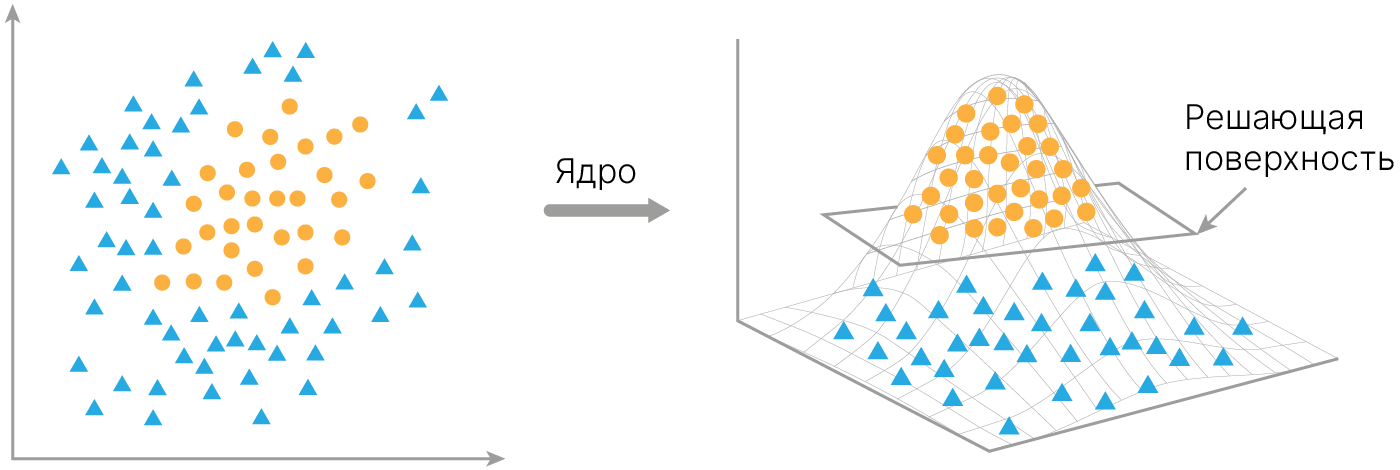
Выше мы ввели $\text{Loss}$ для Hard Margin Classifier:
$$\large \text{Loss} = \frac{1}{2} ||\vec w||^2 + \sum_i \alpha_i [y_i ((\vec w, \vec x_i) + b) - 1],$$где $\alpha_i\geq0$ — множитель Лагранжа. Он будет не равен нулю только для опорных векторов.
С добавлением некоторых математических ограничений эту формулу можно переписать ✏️[blog] в дуальной форме:
$$\large \text{Loss} = \sum_i \alpha_i+ \sum_i \sum_j \alpha_i \alpha_j y_i y_j (\vec x_i, \vec x_j) = \sum_i \alpha_i+ \sum_i \sum_j \alpha_i \alpha_j y_i y_j K(\vec x_i, \vec x_j),$$где $(\vec x_i, \vec x_j)$ — скалярное произведение.
Для получения дуальной формы приравнивают нулю производные $\dfrac {\partial \text{Loss}} {\partial w}$ и $\dfrac {\partial \text{Loss}} {\partial b}$ и подставляют их в исходную формулу.
В этой формуле можно сделать kernel trick — заменить скалярное произведение на некоторую функцию от двух векторов, которую мы будем называть Kernel function.
Важно заметить, что дуальная форма записи для многоклассовой классификации возможна только в случае one vs one.
Для демонстрации возможностей Kernel SVM создадим датасет, который не разделяется линейными моделями. Для этого воспользуемся функцией sklearn.datasets.make_circles.
from sklearn.datasets import make_circles
x, y = make_circles(n_samples=500, factor=0.3, noise=0.05, random_state=42)
Полученный датасет представляет собой две окружности с разными радиусами и общим центром, относящиеся к разным классам.
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
sns.scatterplot(
x=x[:, 0],
y=x[:, 1],
hue=y,
s=50,
ax=ax,
palette=sns.color_palette(["#2DA9E1", "#F9B041"]),
)
plt.show()
Напишем функцию визуализации разделяющего правила для SVM модели:
from matplotlib.colors import ListedColormap
from sklearn.inspection import DecisionBoundaryDisplay
def plot_svm(x, y, clf):
dull_cmap = ListedColormap(["#B8E1EC", "#FEE7D0"])
fig, ax = plt.subplots(1, 1, figsize=(5, 5))
disp = DecisionBoundaryDisplay.from_estimator(
clf,
x,
response_method="predict",
cmap=dull_cmap,
alpha=0.8,
xlabel="feature 1",
ylabel="feature 2",
ax=ax,
)
sns.scatterplot(
x=x[:, 0],
y=x[:, 1],
hue=y,
s=50,
ax=ax,
palette=sns.color_palette(["#2DA9E1", "#F9B041"]),
)
plt.show()
Первое ядро, которое мы рассмотрим, линейное. Оно задается формулой: $$\large K(\vec x_i, \vec x_j) = (\vec x_i, \vec x_j)$$
Линейным ядром является скалярное произведение векторов.
Линейное ядро не способно справиться с такой задачей:
from sklearn import svm
clf = svm.SVC(kernel="linear")
clf.fit(x, y)
plot_svm(x, y, clf)
Следующее ядро, реализованное в библиотеке Sklearn — полиномиальное, оно задается формулой:
$$\large K(\vec x_i, \vec x_j) = (\gamma (\vec x_i, \vec x_j)+r)^d,$$
где $d$ — настраиваемый параметр: степень полинома degree.
Попробуем применить полиномиальное ядро к нашим данным:
clf = svm.SVC(kernel="poly")
clf.fit(x, y)
plot_svm(x, y, clf)
Полиномиальное ядро действует не совсем как полиномиальная модель: $$\large f(\vec wX +b) = (\vec wX +b)^2 = (\vec wX)^2 +2b \vec wX + b^2$$
Kernel SVM не создает новых весов, а перераспределяет веса, которые были у линейной модели.
У модели не получилось разделить данные. Это связано с тем, что значение degree по умолчанию равно 3 (хотя если бы мы взяли "честную” полиномиальную модель, нам бы хватило 2-й степени).
Попробуем увеличить степень полинома:
clf = svm.SVC(kernel="poly", degree=4)
clf.fit(x, y)
plot_svm(x, y, clf)
Вывод который тут стоит сделать: для получения оптимального результата бывает полезным настроить параметры ядра с учетом даных.
Самым популярным ядром SVM является ядро радиальных базисных функций RBF, или гауссово ядро. Оно получено из гауссова распределения, а гауссово распределение характерно для большого количества измеряемых величин. Данное ядро задается формулой:
$$\large K(\vec x_i, \vec x_j) = e^{-\gamma{||\vec x_i - \vec x_j||^2}}$$Настраиваемыми параметрами модели являются C и gamma. C определяет степень гладкости поверхности принятия решений: чем больше C, тем сложнее поверхность и выше вероятность переобучения (про переобучение поговорим ниже). gamma определяет влияние одного обучающего примера (подробнее 🛠️[doc]).
SVM может проверять пространства признаков бесконечного размера, если для такого пространства существует kernel function. RFB ядро как раз соответствует 📚[book] такому случаю бесконечномерного пространства признаков.
clf = svm.SVC(kernel="rbf")
clf.fit(x, y)
plot_svm(x, y, clf)
Также в Sklearn реализовано sigma ядро. Оно интересно больше с исторической точки зрения, т.к. эквивалентно модели нейрона — Перцептрону, о котором вы узнаете на 5-й лекции. На практике 🎓[article] оно в большинстве случаев проигрывает RBF ядру.
Мы уже обсудили, зачем нужна нормализация данных для линейной модели. В данном разделе мы обсудим виды нормализации более подробно.
Загрузим датасет с образцами здоровой и раковой ткани. Датасет состоит из 569 примеров, где каждой строчке из 30 признаков соответствует класс 1 злокачественной (malignant) или 0 доброкачественной (benign) ткани. Задача состоит в том, чтобы по 30-ти признакам обучить модель определять тип ткани (злокачественная или доброкачественная).
import sklearn.datasets
cancer = sklearn.datasets.load_breast_cancer() # load data
x = cancer.data # features
y = cancer.target # labels(classes)
print(f"x shape: {x.shape}, y shape: {y.shape}")
print(f"x[0]: \n {x[0]}")
print(f"y[0]: \n {y[0]}")
x shape: (569, 30), y shape: (569,) x[0]: [1.799e+01 1.038e+01 1.228e+02 1.001e+03 1.184e-01 2.776e-01 3.001e-01 1.471e-01 2.419e-01 7.871e-02 1.095e+00 9.053e-01 8.589e+00 1.534e+02 6.399e-03 4.904e-02 5.373e-02 1.587e-02 3.003e-02 6.193e-03 2.538e+01 1.733e+01 1.846e+02 2.019e+03 1.622e-01 6.656e-01 7.119e-01 2.654e-01 4.601e-01 1.189e-01] y[0]: 0
Быстрее и удобнее можно посмотреть на данные, используя pandas. К тому же Colab добавил возможность визуализации данных (для этого можно тыкнуть синий значок диаграммы ▆ █ ▄ справа от таблицы):
import pandas as pd
cancer_df = pd.DataFrame(data=cancer.data, columns=cancer.feature_names)
cancer_df
| mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | mean fractal dimension | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 17.99 | 10.38 | 122.80 | 1001.0 | 0.11840 | 0.27760 | 0.30010 | 0.14710 | 0.2419 | 0.07871 | ... | 25.380 | 17.33 | 184.60 | 2019.0 | 0.16220 | 0.66560 | 0.7119 | 0.2654 | 0.4601 | 0.11890 |
| 1 | 20.57 | 17.77 | 132.90 | 1326.0 | 0.08474 | 0.07864 | 0.08690 | 0.07017 | 0.1812 | 0.05667 | ... | 24.990 | 23.41 | 158.80 | 1956.0 | 0.12380 | 0.18660 | 0.2416 | 0.1860 | 0.2750 | 0.08902 |
| 2 | 19.69 | 21.25 | 130.00 | 1203.0 | 0.10960 | 0.15990 | 0.19740 | 0.12790 | 0.2069 | 0.05999 | ... | 23.570 | 25.53 | 152.50 | 1709.0 | 0.14440 | 0.42450 | 0.4504 | 0.2430 | 0.3613 | 0.08758 |
| 3 | 11.42 | 20.38 | 77.58 | 386.1 | 0.14250 | 0.28390 | 0.24140 | 0.10520 | 0.2597 | 0.09744 | ... | 14.910 | 26.50 | 98.87 | 567.7 | 0.20980 | 0.86630 | 0.6869 | 0.2575 | 0.6638 | 0.17300 |
| 4 | 20.29 | 14.34 | 135.10 | 1297.0 | 0.10030 | 0.13280 | 0.19800 | 0.10430 | 0.1809 | 0.05883 | ... | 22.540 | 16.67 | 152.20 | 1575.0 | 0.13740 | 0.20500 | 0.4000 | 0.1625 | 0.2364 | 0.07678 |
| ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... | ... |
| 564 | 21.56 | 22.39 | 142.00 | 1479.0 | 0.11100 | 0.11590 | 0.24390 | 0.13890 | 0.1726 | 0.05623 | ... | 25.450 | 26.40 | 166.10 | 2027.0 | 0.14100 | 0.21130 | 0.4107 | 0.2216 | 0.2060 | 0.07115 |
| 565 | 20.13 | 28.25 | 131.20 | 1261.0 | 0.09780 | 0.10340 | 0.14400 | 0.09791 | 0.1752 | 0.05533 | ... | 23.690 | 38.25 | 155.00 | 1731.0 | 0.11660 | 0.19220 | 0.3215 | 0.1628 | 0.2572 | 0.06637 |
| 566 | 16.60 | 28.08 | 108.30 | 858.1 | 0.08455 | 0.10230 | 0.09251 | 0.05302 | 0.1590 | 0.05648 | ... | 18.980 | 34.12 | 126.70 | 1124.0 | 0.11390 | 0.30940 | 0.3403 | 0.1418 | 0.2218 | 0.07820 |
| 567 | 20.60 | 29.33 | 140.10 | 1265.0 | 0.11780 | 0.27700 | 0.35140 | 0.15200 | 0.2397 | 0.07016 | ... | 25.740 | 39.42 | 184.60 | 1821.0 | 0.16500 | 0.86810 | 0.9387 | 0.2650 | 0.4087 | 0.12400 |
| 568 | 7.76 | 24.54 | 47.92 | 181.0 | 0.05263 | 0.04362 | 0.00000 | 0.00000 | 0.1587 | 0.05884 | ... | 9.456 | 30.37 | 59.16 | 268.6 | 0.08996 | 0.06444 | 0.0000 | 0.0000 | 0.2871 | 0.07039 |
569 rows × 30 columns
Colab делает не полную визуализацию признаков, но и на данных изображениях можно найти полезную информацию о выбросах (из графика Values), плотности распределений (из графика Distributions) и о наличии зависимости между переменными (из графика 2-d distributions). Например, мы можем увидеть, что значения признаков mean area и mean perimeter имеют зависимость, близкую к линейной, что не очень хорошо (почему, обсудим позже).
Кроме того, можно тыкнуть на рисунок, посмотреть и скопировать код визуализации, чтобы применить к другим данным или изменить под свои нужды.
Теперь давайте посмотрим на сами данные. У нас есть 569 строк, в каждой из которой по 30 колонок. Такие колонки называют признаками или features. Попробуем математически описать все эти признаки (mean, std, min и тд).
cancer_df.describe()
| mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | mean fractal dimension | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| count | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | ... | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 | 569.000000 |
| mean | 14.127292 | 19.289649 | 91.969033 | 654.889104 | 0.096360 | 0.104341 | 0.088799 | 0.048919 | 0.181162 | 0.062798 | ... | 16.269190 | 25.677223 | 107.261213 | 880.583128 | 0.132369 | 0.254265 | 0.272188 | 0.114606 | 0.290076 | 0.083946 |
| std | 3.524049 | 4.301036 | 24.298981 | 351.914129 | 0.014064 | 0.052813 | 0.079720 | 0.038803 | 0.027414 | 0.007060 | ... | 4.833242 | 6.146258 | 33.602542 | 569.356993 | 0.022832 | 0.157336 | 0.208624 | 0.065732 | 0.061867 | 0.018061 |
| min | 6.981000 | 9.710000 | 43.790000 | 143.500000 | 0.052630 | 0.019380 | 0.000000 | 0.000000 | 0.106000 | 0.049960 | ... | 7.930000 | 12.020000 | 50.410000 | 185.200000 | 0.071170 | 0.027290 | 0.000000 | 0.000000 | 0.156500 | 0.055040 |
| 25% | 11.700000 | 16.170000 | 75.170000 | 420.300000 | 0.086370 | 0.064920 | 0.029560 | 0.020310 | 0.161900 | 0.057700 | ... | 13.010000 | 21.080000 | 84.110000 | 515.300000 | 0.116600 | 0.147200 | 0.114500 | 0.064930 | 0.250400 | 0.071460 |
| 50% | 13.370000 | 18.840000 | 86.240000 | 551.100000 | 0.095870 | 0.092630 | 0.061540 | 0.033500 | 0.179200 | 0.061540 | ... | 14.970000 | 25.410000 | 97.660000 | 686.500000 | 0.131300 | 0.211900 | 0.226700 | 0.099930 | 0.282200 | 0.080040 |
| 75% | 15.780000 | 21.800000 | 104.100000 | 782.700000 | 0.105300 | 0.130400 | 0.130700 | 0.074000 | 0.195700 | 0.066120 | ... | 18.790000 | 29.720000 | 125.400000 | 1084.000000 | 0.146000 | 0.339100 | 0.382900 | 0.161400 | 0.317900 | 0.092080 |
| max | 28.110000 | 39.280000 | 188.500000 | 2501.000000 | 0.163400 | 0.345400 | 0.426800 | 0.201200 | 0.304000 | 0.097440 | ... | 36.040000 | 49.540000 | 251.200000 | 4254.000000 | 0.222600 | 1.058000 | 1.252000 | 0.291000 | 0.663800 | 0.207500 |
8 rows × 30 columns
То же самое, но в виде графика. Видно, что у фич совершенно разные диапазоны значений.
import seaborn as sns
from matplotlib import pyplot as plt
plt.figure(figsize=(6, 5))
ax = sns.boxenplot(
data=cancer_df,
orient="h",
palette="Set2",
linewidth=0.4,
flier_kws={"marker": "o", "s": 3},
line_kws={"linewidth": 1},
)
ax.set(xscale="log", xlim=(1e-4, 1e4), xlabel="Values", ylabel="Features")
plt.show()
Линейная модель представляет собой сумму взвешенных признаков. Если мы приведем признаки к единому масштабу, мы сможем оценить их вклад в модель по значениям весов. Кроме того, работать с признаками в одном диапазоне вычислительно удобно. Для этого будем использовать нормализацию.
Нормализацией называется процедура приведения входных данных к общим значениям математических статистик.
Нормализация строит взаимно однозначное соответствие между некоторыми размерными величинами (которые измеряются в метрах, килограммах, годах и т. п.) и их безразмерными аналогами. Исходные значения можно восстановить, зная статистики оригинальных данных и правило, по которому делалась нормализация.
Часто используют следующие варианты нормализации: MinMaxScaler, StandardScaler, RobustScaler.
Идея MinMaxScaler заключается в том, что он преобразует данные из имеющегося диапазона значений в диапазон от $0$ до $1$. Может быть полезно, если нужно выполнить преобразование, в котором отрицательные значения не допускаются (например, масштабирование RGB пикселей).
где $z_i$ — масштабированное значение, $X_i$ — текущее значение, $X_{\min}$ и $X_{\max}$ — минимальное и максимальное значения имеющихся данных.
Идея StandardScaler заключается в том, что он преобразует данные таким образом, что распределение будет иметь среднее значение $0$ и стандартное отклонение $1$. Большинство значений будет находиться в диапазоне от $-1$ до $1$. Это стандартная трансформация, и она применима во многих ситуациях.
где $u$ — среднее значение (или $0$ при with_mean=False), $s$ — стандартное отклонение (или $0$ при with_std=False).
И StandardScaler, и MinMaxScaler чувствительны к наличию выбросов. RobustScaler использует медиану и основан на процентилях. $k$-й процентиль — это величина, равная или не превосходящая k процентов чисел во всём имеющемся распределении. Например, 50-й процентиль (медиана) распределения таков, что 50% чисел из распределения не меньше данного числа.
Соответственно, RobustScaler не зависит от небольшого числа очень больших предельных выбросов (outliers). Следовательно, результирующий диапазон преобразованных значений признаков больше, чем для предыдущих скэйлеров и, что более важно, примерно одинаков.
где $X_\text{median}$ — значение медианы, $IQR$ — межквартильный диапазон, равный разнице между 75-ым и 25-ым процентилями.
Сравним MinMaxScaler, StandardScaler, RobustScaler для случайного набора признаков.
import random
random.seed(0)
random_names = random.sample(list(cancer.feature_names), 8)
cut_df = cancer_df[random_names]
from sklearn.preprocessing import MinMaxScaler, RobustScaler, StandardScaler
def plot_norm(df, ax, title):
sns.boxenplot(
df,
orient="h",
palette="Set2",
ax=ax,
linewidth=0.2,
flier_kws={"marker": "o", "s": 5},
line_kws={"linewidth": 1},
)
ax.set(xlabel="Values", title=title)
fig, axs = plt.subplots(2, 2, figsize=(10, 7))
plot_norm(cut_df, axs[0][0], "Original")
axs[0][0].set(xscale="log", xlim=(1e-4, 1e4))
min_max_x = MinMaxScaler().fit_transform(cut_df)
plot_norm(pd.DataFrame(min_max_x, columns=random_names), axs[0][1], "MinMax")
std_x = StandardScaler().fit_transform(cut_df)
plot_norm(pd.DataFrame(std_x, columns=random_names), axs[1][0], "Standard")
rob_x = RobustScaler().fit_transform(cut_df)
plot_norm(pd.DataFrame(rob_x, columns=random_names), axs[1][1], "Robust")
plt.subplots_adjust(wspace=0.55, hspace=0.35)
plt.show()
Перед выбором нормализации важно разобраться с природой выбросов. Для этого на выбросы нужно посмотреть с точки зрения эксперта и попробовать определить, являются ли выбросы ошибкой при сборе данных или редкими случаями, которые необходимо сохранить.
Мы не являемся экспертами в медицине и мало знаем о данных, поэтому будем считать, что наши признаки имеют распределение, близкое к нормальному. Поэтому мы будем использовать StandardScaler. StandardScaler часто используют как нормировку по умолчанию.
x_norm = StandardScaler().fit_transform(cancer_df) # scaled data
Видим, что они стали намного более сравнимы между собой.
pd.DataFrame(x_norm, columns=cancer.feature_names).describe()
| mean radius | mean texture | mean perimeter | mean area | mean smoothness | mean compactness | mean concavity | mean concave points | mean symmetry | mean fractal dimension | ... | worst radius | worst texture | worst perimeter | worst area | worst smoothness | worst compactness | worst concavity | worst concave points | worst symmetry | worst fractal dimension | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| count | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | ... | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 | 5.690000e+02 |
| mean | -3.153111e-15 | -6.568462e-15 | -6.993039e-16 | -8.553985e-16 | 6.081447e-15 | -1.136369e-15 | -2.997017e-16 | 1.023981e-15 | -1.860648e-15 | -1.504752e-15 | ... | -2.297713e-15 | 1.742016e-15 | -1.198807e-15 | 6.118909e-16 | -5.094929e-15 | -2.122887e-15 | 6.118909e-16 | -1.998011e-16 | -2.422589e-15 | 2.497514e-15 |
| std | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | ... | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 | 1.000880e+00 |
| min | -2.029648e+00 | -2.229249e+00 | -1.984504e+00 | -1.454443e+00 | -3.112085e+00 | -1.610136e+00 | -1.114873e+00 | -1.261820e+00 | -2.744117e+00 | -1.819865e+00 | ... | -1.726901e+00 | -2.223994e+00 | -1.693361e+00 | -1.222423e+00 | -2.682695e+00 | -1.443878e+00 | -1.305831e+00 | -1.745063e+00 | -2.160960e+00 | -1.601839e+00 |
| 25% | -6.893853e-01 | -7.259631e-01 | -6.919555e-01 | -6.671955e-01 | -7.109628e-01 | -7.470860e-01 | -7.437479e-01 | -7.379438e-01 | -7.032397e-01 | -7.226392e-01 | ... | -6.749213e-01 | -7.486293e-01 | -6.895783e-01 | -6.421359e-01 | -6.912304e-01 | -6.810833e-01 | -7.565142e-01 | -7.563999e-01 | -6.418637e-01 | -6.919118e-01 |
| 50% | -2.150816e-01 | -1.046362e-01 | -2.359800e-01 | -2.951869e-01 | -3.489108e-02 | -2.219405e-01 | -3.422399e-01 | -3.977212e-01 | -7.162650e-02 | -1.782793e-01 | ... | -2.690395e-01 | -4.351564e-02 | -2.859802e-01 | -3.411812e-01 | -4.684277e-02 | -2.695009e-01 | -2.182321e-01 | -2.234689e-01 | -1.274095e-01 | -2.164441e-01 |
| 75% | 4.693926e-01 | 5.841756e-01 | 4.996769e-01 | 3.635073e-01 | 6.361990e-01 | 4.938569e-01 | 5.260619e-01 | 6.469351e-01 | 5.307792e-01 | 4.709834e-01 | ... | 5.220158e-01 | 6.583411e-01 | 5.402790e-01 | 3.575891e-01 | 5.975448e-01 | 5.396688e-01 | 5.311411e-01 | 7.125100e-01 | 4.501382e-01 | 4.507624e-01 |
| max | 3.971288e+00 | 4.651889e+00 | 3.976130e+00 | 5.250529e+00 | 4.770911e+00 | 4.568425e+00 | 4.243589e+00 | 3.927930e+00 | 4.484751e+00 | 4.910919e+00 | ... | 4.094189e+00 | 3.885905e+00 | 4.287337e+00 | 5.930172e+00 | 3.955374e+00 | 5.112877e+00 | 4.700669e+00 | 2.685877e+00 | 6.046041e+00 | 6.846856e+00 |
8 rows × 30 columns
plt.figure(figsize=(6, 5))
ax = sns.boxenplot(
data=pd.DataFrame(x_norm, columns=cancer.feature_names),
orient="h",
palette="Set2",
linewidth=0.4,
flier_kws={"marker": "o", "s": 3},
line_kws={"linewidth": 1},
)
ax.set(xlabel="Values")
plt.show()
Часто может оказаться, что признаковое описание объекта избыточно и между различными признаками имеются связи. Для устойчивости работы линейных моделей важно, чтобы среди признаков не было скоррелированных пар.
Например, если мы будем решать задачу регрессии на наборе признаков $x_1 \dots x_n$, среди которых есть связь $x_2 = 5 x_1$, и возьмём линейную модель вида $$\large y = w_1 x_1 + w_2 x_2 + \dots + w_n x_n + b,$$ то с учётом данной связи мы можем записать: $$\large y = w_1 x_1 + w_2 (5x_1) + \dots + w_n x_n + b = (w_1 + 5 w_2) x_1 + w_3 x_3 + \dots + w_n x_n + b.$$
Таким образом, наша модель теперь учитывает признак $x_1$ с одним "общим" весом $(w_1 + 5 w_2)$, несмотря на то, что он закодирован двумя независимыми параметрами. Решение, то есть набор весовых коэффициентов $w_i$, перестало быть единственным, так как мы теперь можем делать произвольные преобразования с числами $w_1$ и $w_2$ до тех пор, пока $(w_1 + 5 w_2)$ остаётся неизменным:
$$(w_1 + 5 w_2) = \{w_1 \rightarrow w_1 + 5000 ,\, w_2 \rightarrow w_2 - 1000 \} $$$$(w_1 + 5 w_2) = \{w_1 \rightarrow w_1 + 5000000 ,\, w_2 \rightarrow w_2 - 1000000 \} $$$$(w_1 + 5 w_2) = \{w_1 \rightarrow w_1 + 5000000000 ,\, w_2 \rightarrow w_2 - 1000000000 \} $$$$(w_1 + 5 w_2) = \{w_1 \rightarrow w_1 + 5000000000000 ,\, w_2 \rightarrow w_2 - 1000000000000 \} $$$$(w_1 + 5 w_2) = \{w_1 \rightarrow w_1 + Nan ,\, w_2 \rightarrow w_2 + Nan\}$$Чем это плохо?
В случае корреляции признаков задача не имеет единственного решения и не существует обратной матрицы, обеспечивающей аналитическое решение. Мы можем использовать градиентные методы (поговорим позже) для поиска решения, но при этом веса модели могут неконтролируемо расти. При этом суммарный вклад признаков может быть мал.
Мы можем оценивать важность признаков в линейной модели, используя веса перед ними (признаки должны быть нормализованы). Чем больше модуль веса, тем больше вклад. Для коррелированных признаков важность будет переоценена.

Кроме того, нужно помнить, что диапазоны числовых переменных ограничены. При неконтролируемом росте весов значение может выйти за диапазон и превратиться в тыкву Nan.

Что делать?
Визуализировать подобные зависимости можно при помощи построения матрицы попарных корреляций признаков:
import numpy as np
cancer_df = pd.DataFrame(data=cancer.data, columns=cancer.feature_names)
# Compute the correlation matrix
corr = cancer_df.corr()
# Generate a mask for the upper triangle
mask = np.triu(np.ones_like(corr, dtype=bool))
# Set up the matplotlib figure
f, ax = plt.subplots(figsize=(8, 6))
# Generate a custom diverging colormap
cmap = sns.diverging_palette(230, 20, as_cmap=True)
# Draw the heatmap with the mask and correct aspect ratio
sns.heatmap(
corr,
mask=mask,
cmap=cmap,
vmax=1,
vmin=-1,
center=0,
square=True,
linewidths=0.5,
cbar_kws={"shrink": 0.5},
)
plt.show()
В наших данных сильно скоррелированы признаки, характеризующие размеры опухоли (мы могли видеть это выше при визуализации 2-d distributions).
В случае корреляции можно:
Сложность модели (model complexity) — важный гиперпараметр. В частности, для линейных моделей сложность может быть представлена количеством параметров, например, для полиномиальных моделей — степенью полинома.
Сложность модели тесно связана с ошибкой обобщения (generalization error). Ошибка обобщения отличается от ошибки обучения, измеряемой на тренировочных данных, тем, что позволяет оценить обобщающую способность модели, приобретенную в процессе обучения, давать точные ответы на неизвестных ей объектах. Cлишком простой модели не будет хватать количества параметров для обобщения сложной закономерности в данных, что приведёт к большой ошибке обобщения. С другой стороны, избыточная сложность модель также приводит к большой ошибке обобщения за счет того, что в силу своей сложности модель начинает пытаться искать закономерности в шуме, добиваясь большей точности на тренировочных данных, теряя при этом часть обобщающей способности.
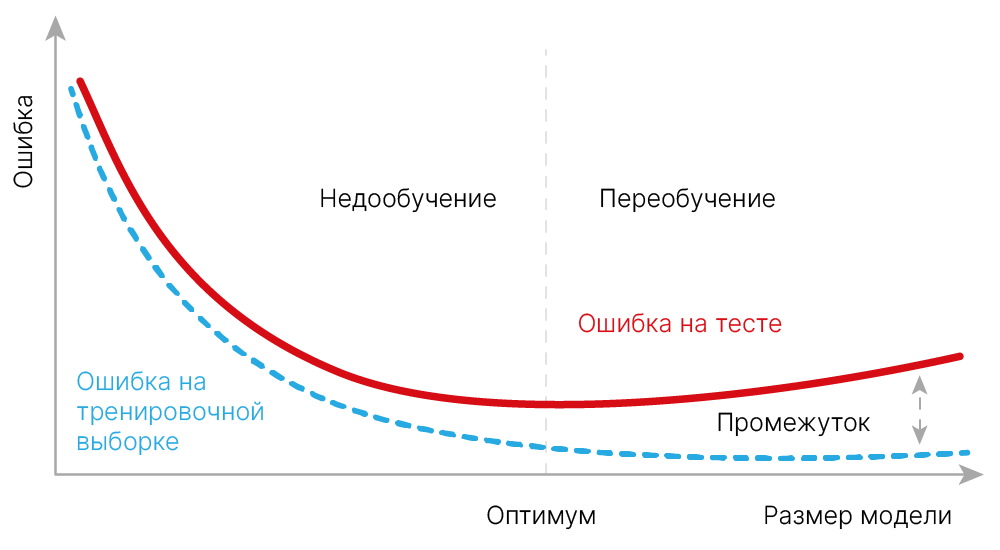
Параметры модели задают некоторую аппроксимацию целевой функции. Аппроксимировать целевую функцию можно несколькими способами, например:
Характерной чертой переобучения является первый сценарий, и сопровождается он, как правило, большими весами.
Проиллюстрируем описанное явление на примере полиномиальной модели:
x = np.linspace(0, 2 * np.pi, 10)
y = np.sin(x) + np.random.normal(scale=0.25, size=len(x))
x_true = np.linspace(0, 2 * np.pi, 200)
y_true = np.sin(x_true)
plt.figure(figsize=(5, 3))
plt.scatter(x, y, s=50, facecolors="none", edgecolors="b", label="noisy data")
plt.plot(x_true, y_true, c="lime", label="ground truth")
plt.legend()
plt.show()
Попробуем аппроксимировать имеющуюся зависимость с помощью полиномиальной модели, используя шумные данные в качестве тренировочных данных:
from sklearn.linear_model import LinearRegression
from sklearn.pipeline import make_pipeline
from sklearn.preprocessing import PolynomialFeatures
x_train = x.reshape(-1, 1)
fig = plt.figure(figsize=(10, 5))
for i, degree in enumerate([0, 1, 3, 9]):
model = make_pipeline(PolynomialFeatures(degree), LinearRegression())
model.fit(x_train, y)
y_plot = model.predict(x_true.reshape(-1, 1))
fig.add_subplot(2, 2, i + 1)
plt.plot(x_true, y_plot, c="red", label=f"M={degree}")
plt.scatter(x, y, s=50, facecolors="none", edgecolors="b")
plt.plot(x_true, y_true, c="lime")
plt.legend()
plt.show()
Видно, что модель может переобучаться, подстраиваясь под тренировочную выборку. В полиноме степень, и, как следствие, количество весов — это гиперпараметр, который можно подбирать на кросс-валидации, однако когда мы таким образом подбираем сложность модели, мы накладываем довольно грубое ограничение на обобщающую способность модели в целом. Вместо этого более разумным было бы оставить модель сложной, но использовать некий ограничитель (регуляризатор), который будет заставлять модель отдавать предпочтение выбору более простого обобщения.
from sklearn.linear_model import Ridge
model = make_pipeline(PolynomialFeatures(9), LinearRegression())
model_ridge = make_pipeline(PolynomialFeatures(9), Ridge(alpha=0.1))
model.fit(x_train, y)
y_plot = model.predict(x_true.reshape(-1, 1))
model_ridge.fit(x_train, y)
y_plot_ridge = model_ridge.predict(x_true.reshape(-1, 1))
plt.figure(figsize=(5, 3))
plt.plot(x_true, y_plot, c="red", label=f"M={degree}")
plt.plot(x_true, y_plot_ridge, c="black", label=f"M={degree}, alpha=0.1")
plt.scatter(x, y, s=50, facecolors="none", edgecolors="b")
plt.plot(x_true, y_true, c="lime", label="ground truth")
plt.legend()
plt.show()
poly_coef = model[1].coef_
eq = f"y = {round(poly_coef[0], 2)}+{round(poly_coef[1], 2)}*x"
for i in range(2, 10):
eq += f"+{round(poly_coef[i], 2)}*x^{i}"
print("Without regularization: ", eq)
poly_coef = model_ridge[1].coef_
eq = f"y = {round(poly_coef[0], 2)}+{round(poly_coef[1], 2)}*x"
for i in range(2, 10):
eq += f"+{round(poly_coef[i], 2)}*x^{i}"
print("With regularization: ", eq)
Without regularization: y = 0.0+-12.11*x+39.41*x^2+-46.31*x^3+28.6*x^4+-10.48*x^5+2.35*x^6+-0.32*x^7+0.02*x^8+-0.0*x^9 With regularization: y = 0.0+0.37*x+0.52*x^2+0.23*x^3+-0.19*x^4+-0.21*x^5+0.17*x^6+-0.04*x^7+0.01*x^8+-0.0*x^9
Видно, что одним из "симптомов" переобучения являются аномально большие веса. Модель Ridge Regression, показанная в примере выше, использует L2-регуляризацию для борьбы с этим явлением:
$$L_2 = \alpha \sum_i w_i^2,$$где $\alpha$ — это коэффициент регуляризации.
Введение L2-регуляризации приводит к тому, что большие веса больше штрафуются и предпочтение отдается решениям, использующим малые значения весов. При этом модель будет сохранять скоррелированные и неважные признаки с маленькими весами.
Это связано с градиентом $L_2$: $$L'_{2w_i} = 2\alpha w_i$$ Он будет “тянуть” модель в сторону маленьких весов.
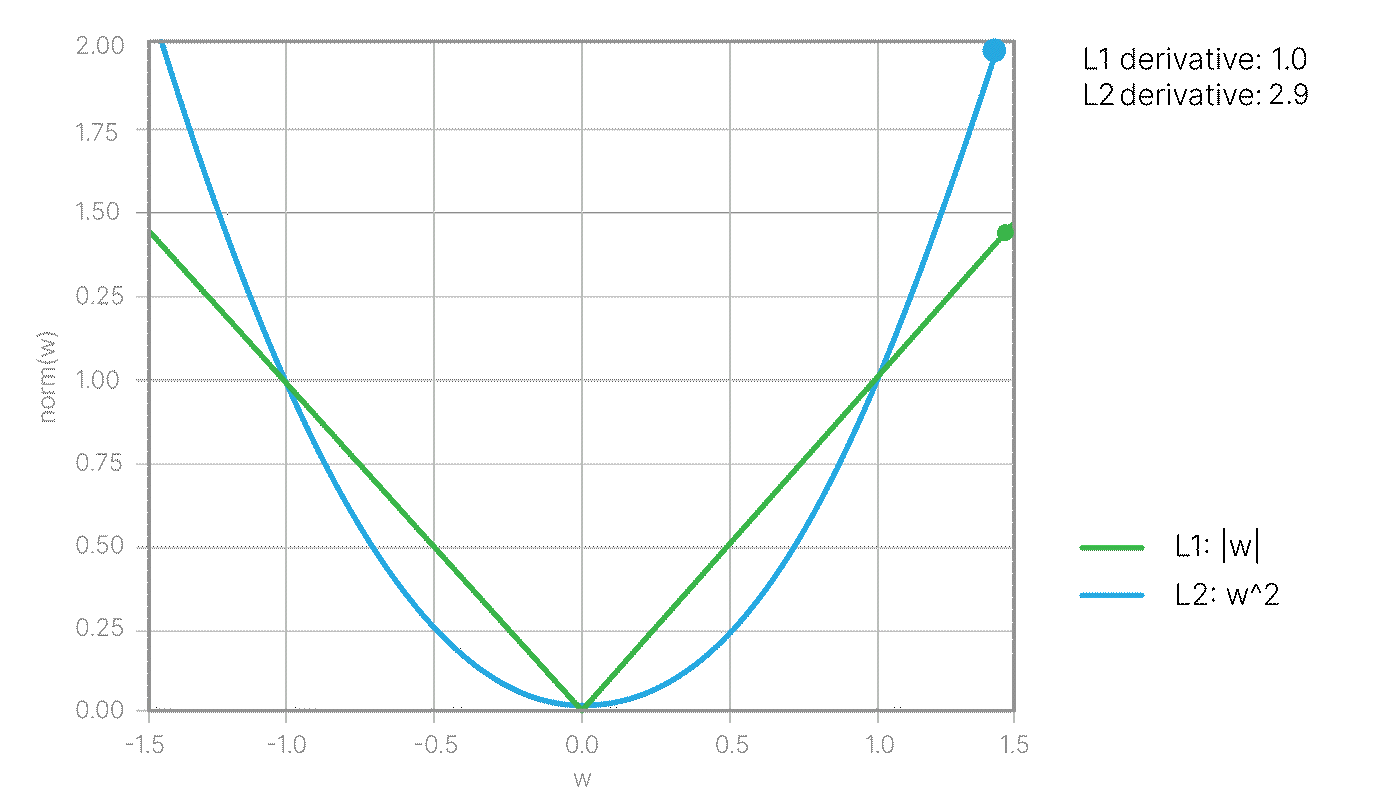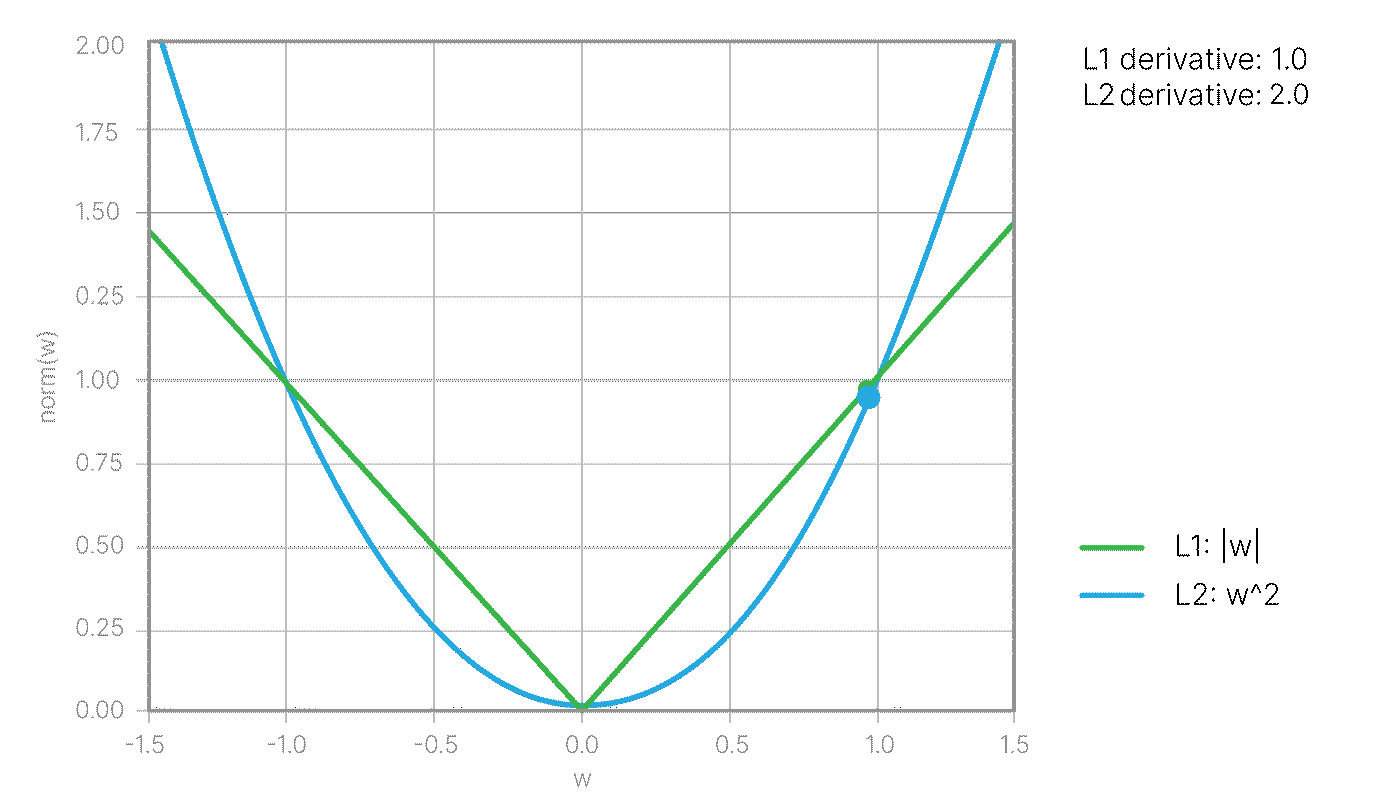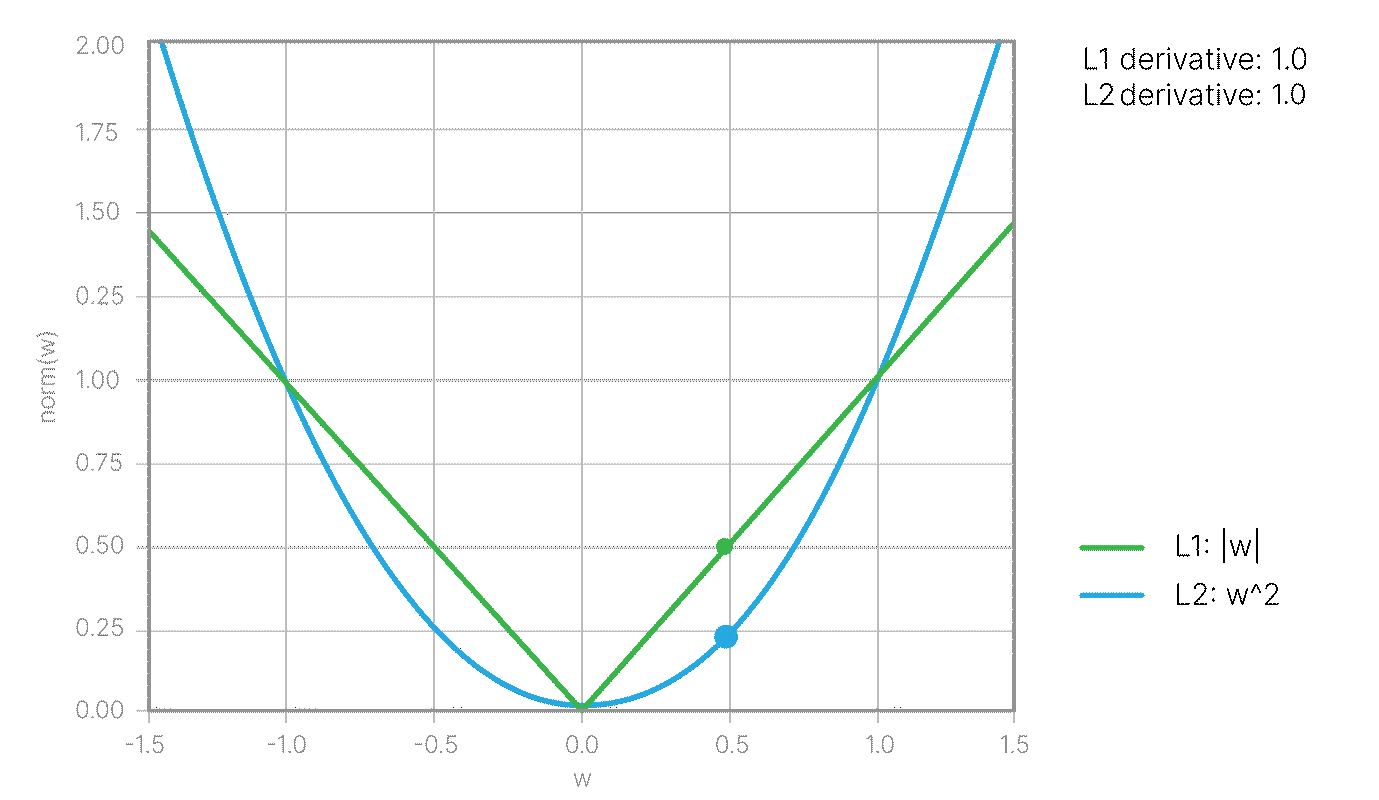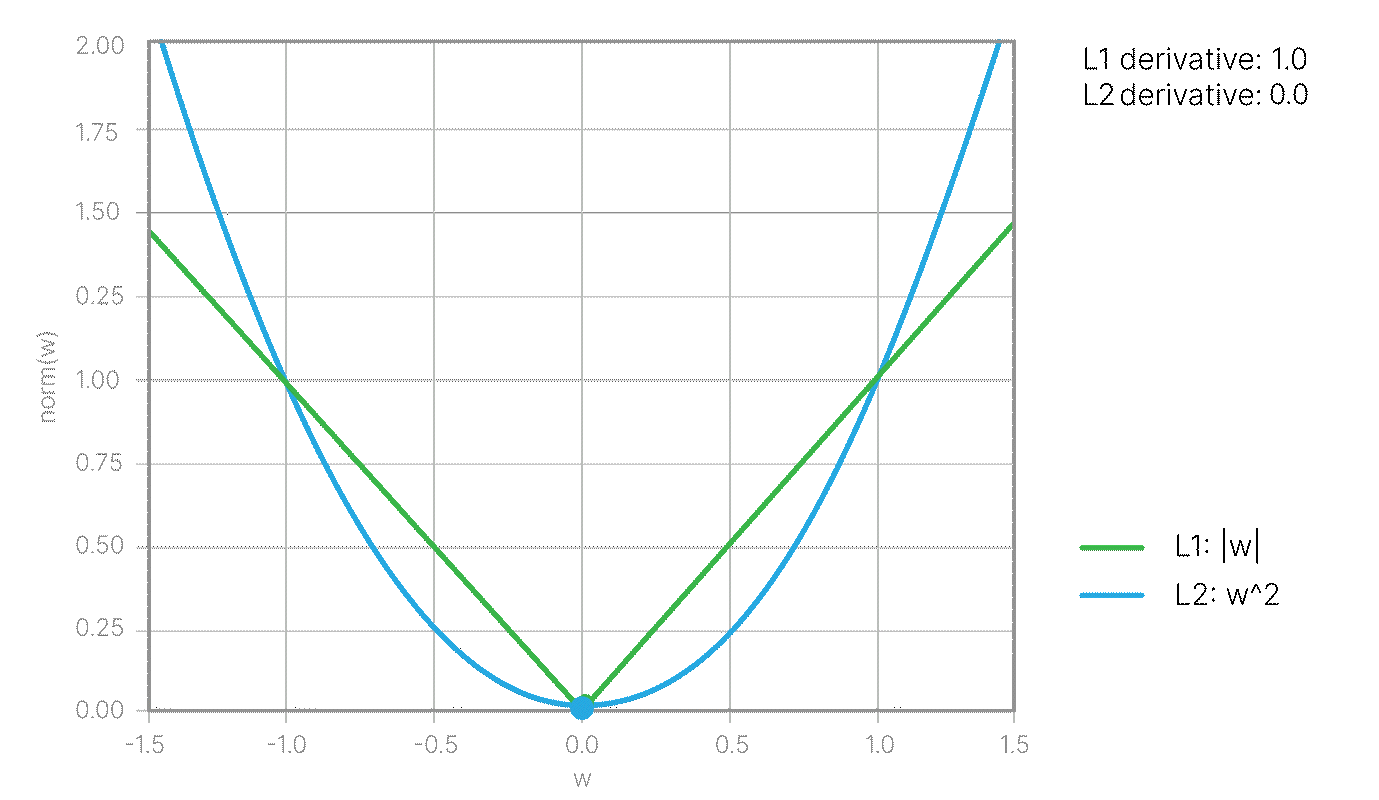
Для отбора признаков можно использовать L1-регуляризацию, она больше штрафует маленькие веса.
$$\large L_1 = \alpha \sum_i |w_i|$$$$\large L_{1w_i}' = \alpha, \text{ где } w_i\neq 0$$L1 одинаково "штрафует" модель за любые ненулевые веса.
Для получения интуиции, что L1-регуляризация позволяет отбирать признаки, обычно используют картинку ниже.
Голубая область — ограничение на значения весов, которое дает регуляризация. Для L2 это окружность. Черная точка — это минимальное значение для функции Loss с регуляризацией. Для L2 она будет лежать на касательной к окружности. Для L1 ограничения на значения весов будут иметь форму ромба. При этом минимальное значение для функции Loss с регуляризацией будет чаще попадать в угол ромба, что соответствует обнулению веса одного из признаков.

Можно построить модель классификатора, которая будет напрямую оценивать вероятность принадлежности объекта к интересующему нас классу просто на основе информации о распределении объектов по классам в обучающей выборке. Базовую идею такого примера легко продемонстрировать на следующих данных.
Загрузим DataFrame датасета Wine 🛠️[doc], который являлся примером табличных данных в первой лекции:
import sklearn
from sklearn.datasets import load_wine
# https://scikit-learn.org/stable/modules/generated/sklearn.datasets.load_wine.html#sklearn.datasets.load_wine
# Download dataset
features, class_labels = load_wine(
return_X_y=True, as_frame=True
) # also we can get data in Bunch (dictionary) or pandas DataFrame
wine_dataset = features
wine_dataset["target"] = class_labels
wine_dataset.head()
| alcohol | malic_acid | ash | alcalinity_of_ash | magnesium | total_phenols | flavanoids | nonflavanoid_phenols | proanthocyanins | color_intensity | hue | od280/od315_of_diluted_wines | proline | target | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 14.23 | 1.71 | 2.43 | 15.6 | 127.0 | 2.80 | 3.06 | 0.28 | 2.29 | 5.64 | 1.04 | 3.92 | 1065.0 | 0 |
| 1 | 13.20 | 1.78 | 2.14 | 11.2 | 100.0 | 2.65 | 2.76 | 0.26 | 1.28 | 4.38 | 1.05 | 3.40 | 1050.0 | 0 |
| 2 | 13.16 | 2.36 | 2.67 | 18.6 | 101.0 | 2.80 | 3.24 | 0.30 | 2.81 | 5.68 | 1.03 | 3.17 | 1185.0 | 0 |
| 3 | 14.37 | 1.95 | 2.50 | 16.8 | 113.0 | 3.85 | 3.49 | 0.24 | 2.18 | 7.80 | 0.86 | 3.45 | 1480.0 | 0 |
| 4 | 13.24 | 2.59 | 2.87 | 21.0 | 118.0 | 2.80 | 2.69 | 0.39 | 1.82 | 4.32 | 1.04 | 2.93 | 735.0 | 0 |
Датасет содержит объекты 3 различных классов:
wine_dataset.target.unique()
array([0, 1, 2])
Возьмём первый признак alcohol. По имеющийся таблице с данными легко построить функцию распределения $f(x)$, которая будет задавать вероятность $p(\text{alcohol} = x)$, и найти среди наших данных бутылку вина с параметром alcohol, равным $x$ (рисунок слева).
Т.к. у нас три класса, мы можем построить распределение объектов в обучающей выборке по признаку alcohol отдельно для каждого из этих трёх классов. Эти распределения зададут нам условную вероятность $p(\text{alcohol} = x |\text{target} = i)$ того, что объект имеет значение признака alcohol, равное $x$, при условии, что он относится к одному из классов с номером $i$ (рисунок справа).
import seaborn as sns
import matplotlib.pyplot as plt
fig, axes = plt.subplots(1, 2, figsize=(12, 5))
sns.kdeplot(wine_dataset, x="alcohol", fill=True, ax=axes[0])
axes[0].set_title("p(alcohol=x)")
sns.kdeplot(
wine_dataset,
x="alcohol",
hue="target",
palette=sns.color_palette(["#5D5DA6", "#2DA9E1", "#F9B041"]),
fill=True,
ax=axes[1],
)
axes[1].set_title("p(alcohol=x|target=i)")
plt.show()
Посмотрев на плотности распределений по классам (рисунок справа), мы можем предположить, что бутылка с значением $\text{alcohol} = 11.3$ будет относиться к 1 классу.
На языке формул наш “метод пристального вглядывания” можно записать с помощью формулы для условной вероятности по теореме Байеса 📚[wiki]:
$$\large p(\text{target} = i | \text{alcohol} = x) = \frac{p(\text{alcohol} = x | \text{target} = i )p(\text{target} = i )}{p(\text{alcohol} = x)},$$где $p(\text{target} = i)$ — доля объектов класса $i$ в датасете, а $p(\text{target} = i | \text{alcohol} = X)$ — вероятность того, что объект принадлежит классу $i$, при условии того, что признак alcohol у него принимает значение $X$.
Мы поняли, откуда в названии метода Байес, теперь разберемся, почему он “наивный”.
Мы использовали только один признак: alcohol. Всего же у нас 13 признаков.
“Наивность” Байеса состоит в том, что эта модель будет рассматривать признаки как независимые случайные величины: $$\large p(\text{features} = \vec x)=p(\text{feature}_1 = x_1)\cdotp(\text{feature}_2 = x_2)...(\text{feature}_n = x_n)$$
Если мы решаем задачу классификации на $k$ классов, то для объекта с набором признаком $\vec x$ по формуле выше мы получим $k$ чисел, характеризующих вероятность принадлежности данного объекта к различным классам. Для финального принятия решения нам останется выбрать тот класс, для которого вероятность принадлежности наивысшая:
$$\large \text{prediction} = \underset{i}{\text{argmax}}{\left(p(\text{target} = i |\text{features} = \vec x )\right)}.$$Вернёмся к нашему датасету Wine и попробуем решить задачу классификации для него при помощи предложенного алгоритма.
Как обычно, разделим наш датасет на тренировочную и валидационную выборки:
from sklearn.model_selection import train_test_split
# Split the data into train and test data
x_train, x_test, y_train, y_test = train_test_split(
features.values, class_labels.values, test_size=0.25, random_state=42
)
Возьмём реализацию Наивного Байесовского классификатора из библиотеки Sklearn 🛠️[doc]. Обучим её на тренировочном датасете и измерим качество на отложенной валидационной выборке:
from sklearn.metrics import f1_score
from sklearn.naive_bayes import GaussianNB
# Train the model
model = GaussianNB()
model.fit(x_train, y_train)
# Calculate F1_score
pred = model.predict(x_test)
f1_score(y_test, pred, average="macro")
1.0
Благодаря простоте модельного датасета Wine наша наивная статистическая модель показала отличное качество работы. Это связано с “простотой” датасета — признаки классов имеют унимодальные распределения (один пик на плотности распределения), для более сложных данных (многомодальные распределения) такого не будет.
Тем не менее, подход к решению задачи классификации, связанный с построением модели предсказания принадлежности объекта к имеющимся классам, оказался конструктивным.
Наивный Байесовский классификатор часто используют в задаче обнаружения спама, и пример его использования в такой задаче может показаться ещё более наглядным.
В рамках данной задачи у нас имеются:
На основе этой информации нам нужно научиться отделять нормальные письма от спама. Все письма состоят из 4-х слов: ‘Добрый’, ‘День’, ‘Гости’, ‘Деньги’. При этом мы уже посчитали, сколько раз каждое слово встречается в каждом классе.
Мы можем посчитать вероятность встретить слово ‘Добрый’ в нормальном письме: берем количество слов ‘Добрый’ и делим на количество слов во всех нормальных письмах (с повторениями). Аналогично для других слов.
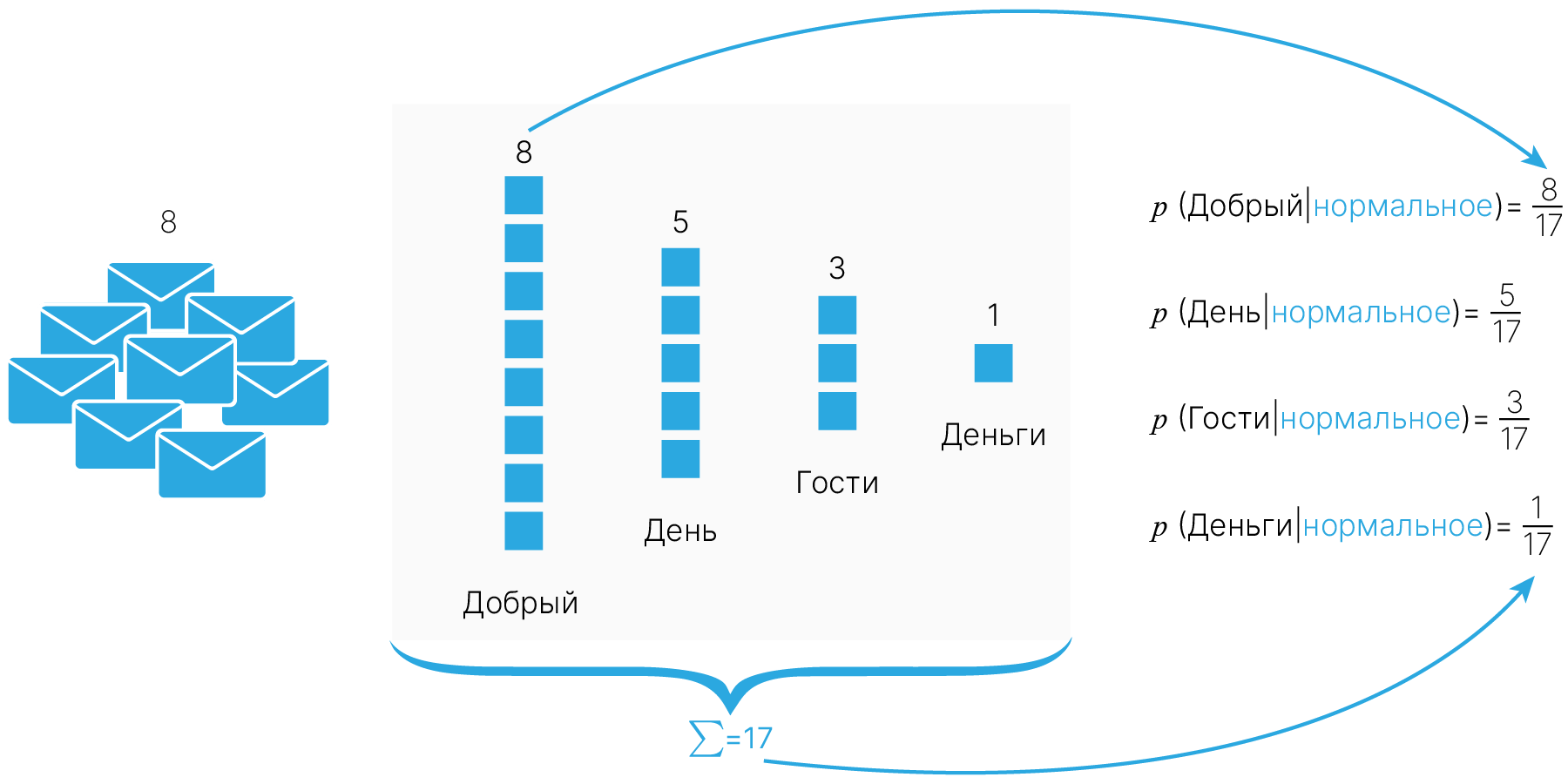
Делаем то же самое для слов из спама.
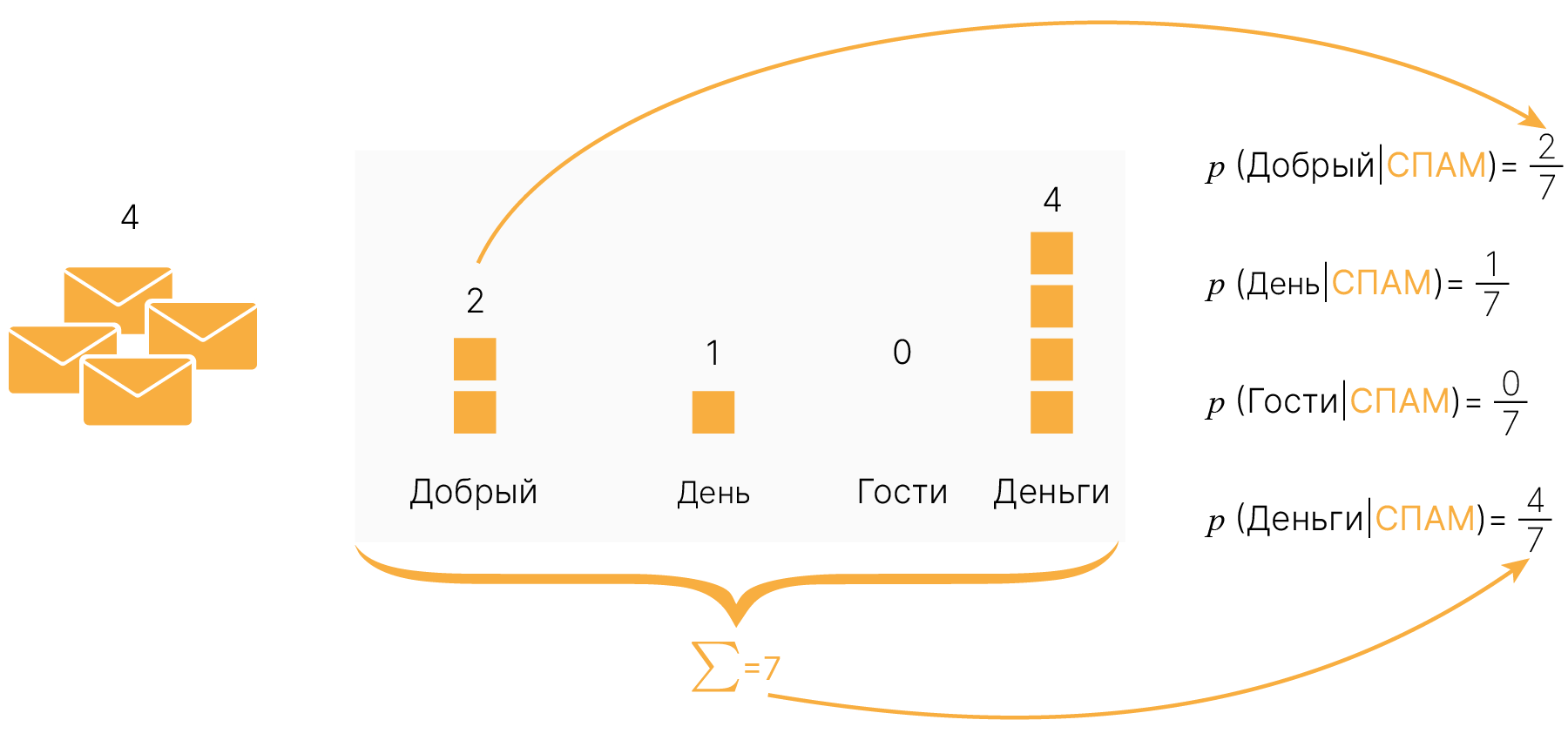
Считаем вероятность того, чтобы письмо было нормальным. Для этого количество нормальных писем делим на общее количество писем. Аналогично для спама. Это $p(\text{target} = i)$ в формуле выше.
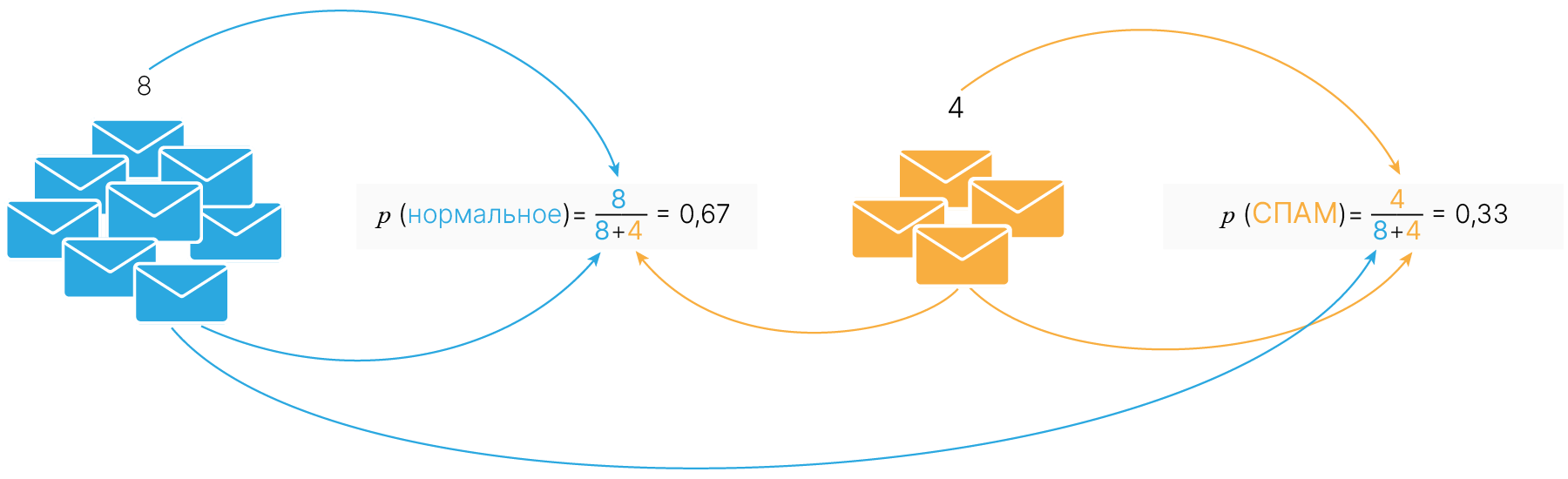
Чтобы получить вероятность нормального письма с фразой ‘Добрый День’ в "наивном" предположении, мы можем перемножить вероятности нормального письма со словом ‘Добрый’ и нормального письма со словом ‘День’. Это произведение будет $p(\text{target} = i | \text{Features} = \vec X)$ в формуле выше.
Считаем $p(\text{Features} = \vec X|\text{target} = i) p(\text{target} = i)$:

Если вы работаете с NLP, советуем ознакомиться с Latent Dirichlet Allocation:
Начнем с задачи бинарной классификации. Линейная модель задается уравнением: $$s = f(\vec x) = (\vec{w}, \vec{x}) + b$$
Выходы такой модели принимают значения от $-∞$ до $+∞$.
Нам бы хотелось получить на выходе вероятность того, что объект принадлежит к классу $1$. Вероятность принимает значения от $0$ до $1$. Нам нужна функция, которая спроецирует диапазон $(-∞,+∞)$ в диапазон $[0, 1]$.
Такой функцией является сигмоида: $$p = \sigma(s) = \frac{1}{1+e^{-s}}$$
При $s→-∞$: $p→0$.
При $s→+∞$: $p→1$.
При $s=0$: $p=0.5$.
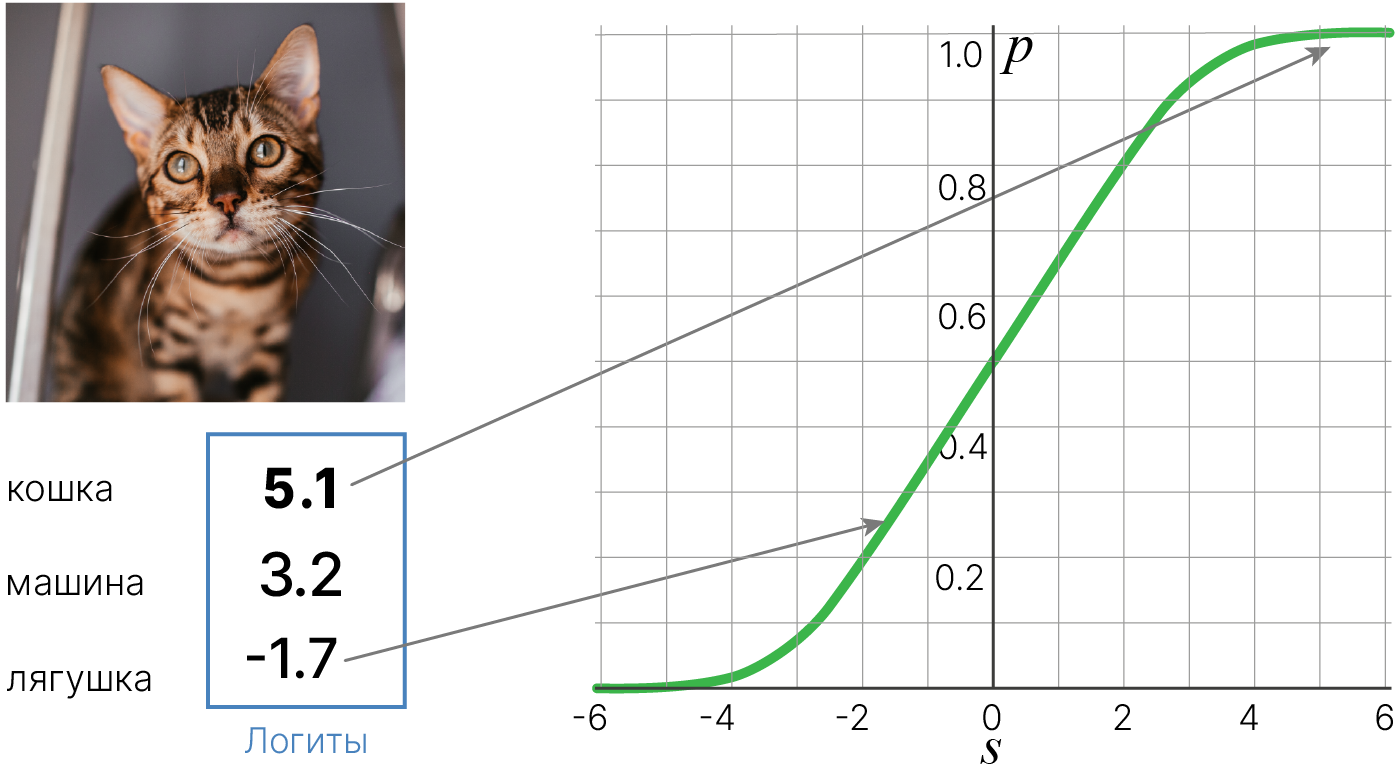
Значения $s$ (score) также называют logit-ом 📚[wiki] (пер. “логарифм”). Это связано с тем, что если выразить logit $s$ через вероятность $p$, то получится формула: $$s(p) = \log \left(\frac{p}{1-p}\right)$$
[video] 📺 Объяснение SoftMax от StatQuest
В случае многоклассовой классификации мы будем считать по logit-у для каждого класса: $$\begin{matrix} s_1 = (\vec{w_1}, \vec{x}) + b_1\\ s_2 = (\vec{w_2}, \vec{x}) + b_2\\ ... \\ s_n = (\vec{w_n}, \vec{x}) + b_n \end{matrix}$$
Для непересекающихся классов результатом классификации будет класс, соответствующий наибольшему logit-у.
Предположим, что наша модель выдала следующие значения:
logits = [[
5.1, # cat
3.2, # car
-1.7, # frog
]]
Тогда, чтобы узнать, какой класс наша сеть предсказала, мы могли бы просто взять argmax от наших logits:
import numpy as np
print("Predicted class = %i (Cat)" % (np.argmax(logits, axis=1).squeeze()))
Predicted class = 0 (Cat)
От argmax нельзя посчитать градиент, так как производная от константы равна 0. Соответственно, если бы мы вставили производную от argmax в градиентный спуск, мы бы получили везде нули, и наша модель бы вообще ничему не научилась.
Кроме того, мы бы хотели получить не logit’ы, а настоящую вероятность $p$ на выходе модели. Да еще и таким образом, чтобы от наших вероятностей можно было посчитать градиент. Для этого мы можем применить к нашим логитам функцию SoftMax: $$\large p(y=k|x=x_i) = \frac{e^{s_k(x_i)}}{\sum_{j=1}^ne^{s_j(x_i)}},$$
где $x_i$ — набор признаков, характеризующий один объект из выборки, $s_j(x_i)$ — logit для j-го класса для объекта $x_i$.
Для этого возведем экспоненту (число Эйлера $e=2.71828$) в степень логита. В результате мы получим вектор гарантированно неотрицательных чисел (положительное число, возведенное в степень, даже отрицательную, даст положительное значение).
Мы должны их нормализовать, то есть поделить на сумму.
Это преобразование называется SoftMax функцией. Получаются вероятности, то есть числа, которые можно интерпретировать, как вероятности.
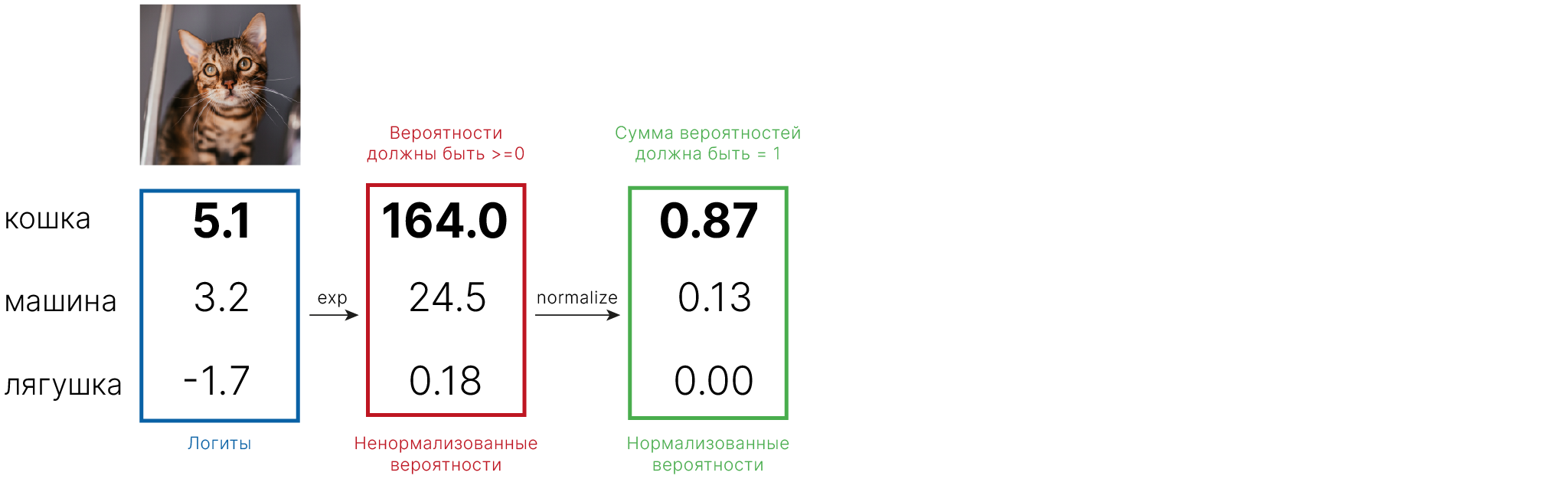
$\displaystyle \text{SoftMax}_\text{кошка} = \frac{e^{5.1}}{e^{5.1} + e^{3.2} + e^{-1.7}}$
def softmax(logits):
return np.exp(logits) / np.sum(np.exp(logits), axis=1, keepdims=True)
print(softmax(logits))
print("Sum = %.2f" % np.sum(softmax(logits)))
[[0.86904954 0.12998254 0.00096793]] Sum = 1.00
Можно обратить внимание, что SoftMax никоим образом не поменял порядок значений. Самому большому logit'у соответствует самая большая вероятность, а самому маленькому, соответственно, самая маленькая.
При вычислении экспоненты от выходов модели могут получиться очень большие числа в силу очень высокой скорости роста экспоненты. Этот факт необходимо учитывать, чтобы вычисления SoftMax были численно стабильны:
from warnings import simplefilter
simplefilter("ignore", category=RuntimeWarning)
f = np.array([123, 456, 789])
p = np.exp(f) / np.sum(np.exp(f))
print(f"logits = {f},\nprobabilities = {p}")
logits = [123 456 789], probabilities = [ 0. 0. nan]
Чтобы регуляризовать вычисление, нам следует предварительно упростить возникающую в вычислении дробь. Для этого мы можем вычесть из каждого $s_i$ положительную константу, чтобы уменьшить значения экспонент. В качестве константы можно выбрать максимальный элемент этого вектора, тогда у нас гарантированно не будет очень больших чисел, и такой способ будет работать более стабильно.
$$M = \max_j s_{j}(x_i),$$$$s^{new}_{j}(x_i) = s_{j}(x_i) - M,$$$$ \dfrac {e^{s^{new}_{k}(x_i)}} {\sum_j e^{s^{new}_{j}(x_i)}} = \dfrac {e^{s_{k}(x_i) - M }} {\sum_j e^{s_{j}(x_i) - M }} = \dfrac {e^{s_{k}(x_i)}e ^ {-M}} {\sum_j e^{s_{j}(x_i)} e ^ {-M}} = \dfrac {e ^ {-M} e^{s_{k}(x_i)}} {e ^ {-M} \sum_j e^{s_{j}(x_i)} } = \dfrac { e^{s_{k}(x_i)}} { \sum_j e^{s_{j}(x_i)} },$$где $x_i$ — набор признаков, характеризующий один объект из выборки, $s_j(x_i)$ — logit для j-го класса для объекта $x_i$.
f = np.array([123, 456, 789])
f -= f.max()
p = np.exp(f) / np.sum(np.exp(f))
print(f"new logits = {f},\nprobabilities = {p}")
new logits = [-666 -333 0], probabilities = [5.75274406e-290 2.39848787e-145 1.00000000e+000]
Теперь нам нужно решить, какую функцию потерь использовать. Вероятности принимают значения от $0$ до $1$. Если мы будем использовать Hinge loss или MSE, максимальным значением ошибки на указанном диапазоне будет $1$. А нам хочется максимально штрафовать модель, если она выдает неправильный класс с вероятностью $1$.
Cross-entropy / log loss

Преимуществом Cross-Entropy loss (зеленый) по сравнению с кусочно-гладкой Hinge Loss (оранжевый) являются:
Чтобы понять, откуда взялась Cross-Entropy, рассмотрим сначала расстояние Кульбака — Лейблера.
В математической статистике и теории информации мерой расхождения между двумя вероятностными распределениями $P$ и $Q$ является расстояние (дивергенция) Кульбака — Лейблера, вычисляемое по формуле: $$D_{KL}(P||Q) = ∑_i P(i)\log\frac{P(i)}{Q(i)}$$
Попробуем разобраться, что значит эта формула, на примере двух монеток:
Возьмем настоящую монету и произведем 10 бросков (выборок). Получили последовательность $\color{blue}{O O} \color{green}{P} \color{blue}{O O} \color{green}{P} \color{blue}{O O O} \color{green}{P}$, где $\color{blue}{O}$ — это орел, $\color{green}{P}$ — это решка. Посчитаем вероятности выбросить такую последовательность для настоящей и фальшивой монеты. Броски независимые, поэтому значения вероятностей перемножаются.

Запишем пропорцию вероятностей данной комбинации для настоящей монетки и для фальшивой (независимые случайные величины, вероятности перемножаются). Для заданных значений вероятностей пропорция будет примерно $149:1$. При пропорции $1:1$ монетки будут идентичны.
$$\frac{\color{blue}{p_1^{N_о}}\color{green}{p_2^{N_р}}} {\color{blue}{q_1^{N_о}}\color{green}{q_2^{N_р}}}= \frac{\color{blue}{\left(\frac{1}{2}\right)^{7}}\color{green}{\left(\frac{1}{2}\right)^{3}}} {\color{blue}{\left(\frac{1}{5}\right)^{7}}\color{green}{\left(\frac{4}{5}\right)^{3}}}\approx \frac{149}{1}$$Возьмем логарифм от этого значения (это позволит нам избавиться от степеней и заменить умножение сложением) и нормируем на количество бросков монетки $N=\color{blue}{N_о}+\color{green}{N_р}$.
$$\frac{\color{blue}{N_о}}{N}\log{\color{blue}{p_1}}+ \frac{\color{green}{N_р}}{N}\log{\color{green}{p_2}}- \frac{\color{blue}{N_о}}{N}\log{\color{blue}{q_1}}- \frac{\color{green}{N_р}}{N}\log{\color{green}{q_2}}$$При увеличении количества бросков $N\to∞$, так как мы бросали настоящую монетку
$$\frac{\color{blue}{N_о}}{N} \to \color{blue}{p1}, \frac{\color{green}{N_р}}{N} \to \color{green}{p2} .$$Получаем расстояние Кульбака — Лейблера.
$$D_{KL}(P||Q) = \color{blue}{p_1} \log{\color{blue}{p_1}} + \color{green}{p_2}\log{\color{green}{p_2}} - \color{blue}{p_1}\log{\color{blue}{q_1}} - \color{green}{p_2}\log{\color{green}{q_2}}$$$$ = \color{blue}{p_1} \log{\color{blue}{\frac{p_1}{q_1}}} + \color{green}{p_2} \log{\color{green}{\frac{p_2}{q_2}}}$$Посмотрим на разные фальшивые монетки
def KL_dist(q1, q2, p1=0.5, p2=0.5):
return p1 * np.log(p1 / q1) + p2 * np.log(p2 / q2)
print(f"q1 = 0.1, q2 = 0.9, Dkl = {KL_dist(0.1, 0.9):0.3f}")
print(f"q1 = 0.2, q2 = 0.8, Dkl = {KL_dist(0.2, 0.8):0.3f}")
print(f"q1 = 0.3, q2 = 0.7, Dkl = {KL_dist(0.3, 0.7):0.3f}")
print(f"q1 = 0.4, q2 = 0.6, Dkl = {KL_dist(0.4, 0.6):0.3f}")
print(f"q1 = 0.5, q2 = 0.5, Dkl = {KL_dist(0.5, 0.5)}")
q1 = 0.1, q2 = 0.9, Dkl = 0.511 q1 = 0.2, q2 = 0.8, Dkl = 0.223 q1 = 0.3, q2 = 0.7, Dkl = 0.087 q1 = 0.4, q2 = 0.6, Dkl = 0.020 q1 = 0.5, q2 = 0.5, Dkl = 0.0
Обратим внимание, что если $P=Q$, то
$$D_{KL}(P||Q) = ∑_i P(i)\log\frac{P(i)}{Q(i)} = 0$$Мы научились определять близость двух распределений. Как это поможет нам оценить качество модели, если мы знаем, какие метки классов должны получиться?
Пусть $P$ — вероятности истинных меток классов для объекта (1 для правильного класса, 0 для остальных), $Q(\theta)$ — вероятности классов для объекта, предсказанные моделью с обучаемыми параметрами $\theta$.
Расстояние Кульбака — Лейблера между истинными и предсказанными значениями:
$$D_{KL}(P||Q(\theta)) = ∑_i P(i)\log\frac{P(i)}{Q(i| \theta)} =$$$$ = ∑_i P(i)\log{P(i))} - ∑_i P(i)\log{Q(i|\theta)} =$$$$ = - H(P) + H(P|Q(\theta))$$Мы разбили сумму на две части, первая из которых называется энтропией $H(P)$ и не будет зависеть от модели, а вторая называется кросс-энтропией $H(P|Q(\theta))$.
Понятие энтропии пришло из теории связи. Для расчета энтропии можно использовать формулу Шеннона:
$$H(P)=-\sum^C_{i=1}P(i)\cdot \log_{2}(P(i)),$$где $C$ — количество классов.
В формуле Шеннона не случайно используется логарифм по основанию 2. Она рассчитывает, сколько бит информации минимально необходимо для передачи одного значения, например, одного исхода броска монетки.
Если монетка всегда выдает орел, то нам нет смысла передавать информацию, чтобы предсказать исход
$$H(\color{blue}{p_1 = 1}, \color{green}{p_2 = 0}) = 0$$Для настоящей монетки необходимо будет передавать 1 бит информации на бросок $$H(\color{blue}{p_1 = 0.5}, \color{green}{p_2 = 0.5})= \log_{2}(2) = 1,$$
А вот с поддельной монеткой получается интереснее: если сделать много бросков, можно выявить закономерность, что решка выпадет чаще (вероятность трех решек подряд будет больше вероятности одного орла), и за счет этого сократить количество передаваемой информации так, чтобы на один бросок получалось меньше 1 бита. Как это сделать — отдельная область теории информации, называемая кодирование источника. $$H(\color{blue}{q_1 = 0.2}, \color{green}{q_2 = 0.8}) = 0.722$$
Энтропия — мера неуверенности, связанная с распределением $P$. Зная истинное распределение случайной величины, мы можем рассчитать его энтропию.
Если мы попытаемся использовать статистические данные, полученные для фальшивой монеты $Q$, для настоящей $P$, мы не получим выигрыш в количестве передаваемой информации:
$$H(P||Q) = - \sum^C_{i=1}P(i)\cdot \log_2(Q(i)) = 1.322$$Формула выше называется кросс-энтропия.
Кросс-энтропия позволяет оценить ситуацию, когда мы аппроксимируем истинное распределение $P$ предсказанным распределением $Q$. Чем больше значения кросс-энтропии, тем больше расхождение между распределениями. Поэтому кросс-энтропию используют в качестве функции потерь.
Как мы показали выше, кросс-энтропия связана с энтропией и расстоянием Кульбака — Лейблера $$H(P||Q) = D_{KL}(P||Q) + H(P).$$
Посчитаем значения для наших монеток с помощью кода:
# normal coin
p1 = 0.5
p2 = 0.5
# fake coin
q1 = 0.2
q2 = 0.8
# Kullback–Leibler divergence
div_kl = p1 * np.log2(p1 / q1) + p2 * np.log2(p2 / q2)
print(f"Dkl(P||Q) = {div_kl:.3f}")
# Entropy normal coin
h_p = -p1 * np.log2(p1) - p2 * np.log2(p2)
print(f"H(P) = {h_p:.3f}")
# Entropy fake coin
h_q = -q1 * np.log2(q1) - q2 * np.log2(q2)
print(f"H(Q) = {h_q:.3f}")
# Cross-entropy
h_p_q = -p1 * np.log2(q1) - p2 * np.log2(q2)
print(f"H(P||Q) = {h_p_q:.3f}")
print(f"H(P||Q) = Dkl(P||Q) + H(P) = {h_p+div_kl:.3f}")
Dkl(P||Q) = 0.322 H(P) = 1.000 H(Q) = 0.722 H(P||Q) = 1.322 H(P||Q) = Dkl(P||Q) + H(P) = 1.322
Вернемся к задаче классификации изображений. Рассчитаем для предсказания модели Cross-Entropy loss.
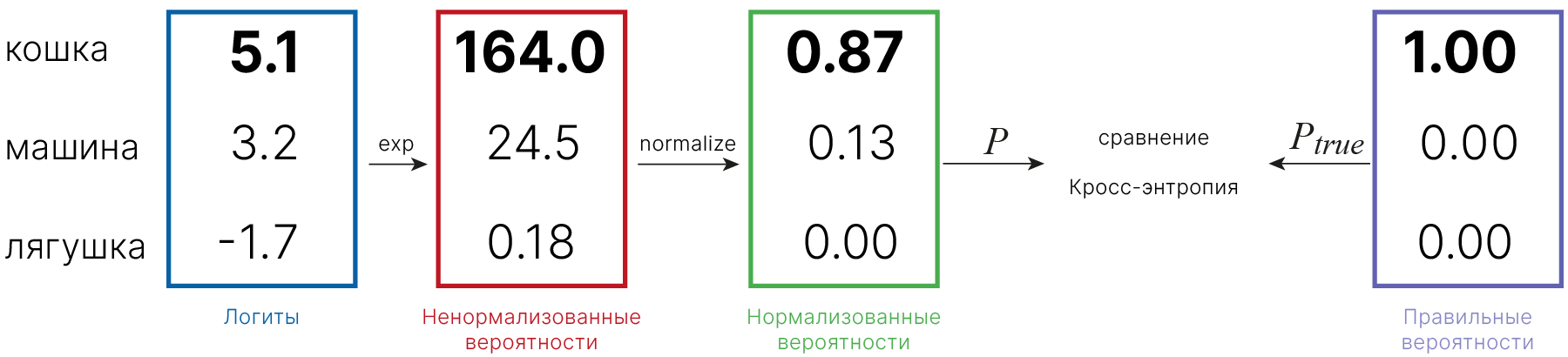
На картинке на входе был изображен кот. Метки классов преобразуются следующим образом: $$ y_i = \begin{cases} 1 & \text{для i=k, где k - номер истинного класса}, \\0 & \text{для любого } i\neq k. \end{cases}$$ Таким образом $$ y = [1, 0, 0]$$
То есть в расчете Loss мы будем использовать только вероятность истинного класса.
В расчетах выше мы использовали логарифм по основанию 2, что приближало нас к теории информации. Мы можем считать кросс-энтропию по натуральному логарифму, она будет отличаться умножением на константу.
$$H(P||y)= - \sum^C_{i=1}y_i\cdot \log(p_i) = -1⋅\log{0.87}-0\cdot\log{0.13}-0\cdot\log{0.001} = - \log(p_{cat}) = - \log{0.87} \approx0.14$$def cross_entropy_loss(pred_prob, true_prob):
return np.sum(-true_prob * np.log(pred_prob)) / pred_prob.shape[0]
# 3 classes 2 items
logits = np.array([
[5.1, 3.2, -1.7], # one item
#[2.1, 6.3, 1.5], # second item
])
print(f"Logits = \n{logits}\n")
pred_prob = softmax(logits)
print(f"Predicted Probabilities = \n{pred_prob}\n")
# 3 classes 2 items
true_prob = np.array([
[1.0, 0.0, 0.0], # one item
#[0.0, 1.0, 0.0], # second item
])
print(f"True Probabilities = \n{true_prob}\n")
print(f"Cross-entropy loss = {cross_entropy_loss(pred_prob, true_prob):.3f}")
Logits = [[ 5.1 3.2 -1.7]] Predicted Probabilities = [[0.86904954 0.12998254 0.00096793]] True Probabilities = [[1. 0. 0.]] Cross-entropy loss = 0.140
Итоговая последовательность преобразований будет выглядеть так:
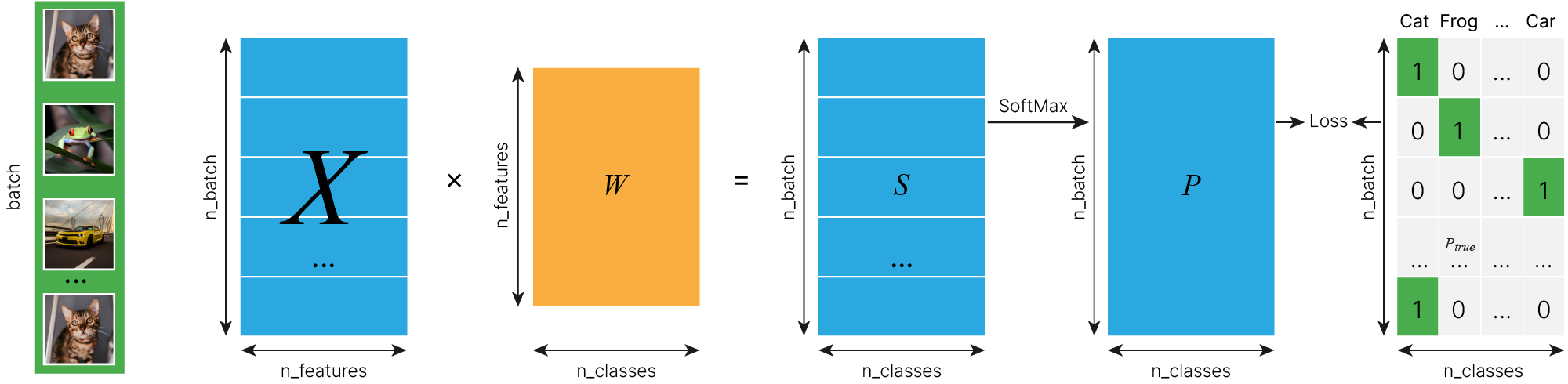
Посчитаем производную от функции ошибок. Функция ошибок:
$$ L = - \sum_i y_i \log p_i = -\sum_i y_i \log(\dfrac {e^{s_{y_i}}} {\sum_j e^{s_{y_j}}}),$$где $s_{y_i}$ — это логиты классов, получаемые из линейной модели:
$$s_{y_i} = w_i x$$Для расчета градиента будем использовать chain rule:
$$ \dfrac {\partial L} {\partial w_i} = \dfrac {\partial L} {\partial s_{y_i}} \dfrac {\partial s_{y_i}} {\partial w_i} $$Градиент логитов по весам:
$$\dfrac {\partial s_{y_i}} {\partial w_i} = x$$У нас только одна истинная метка класса $y_k = 1$, для $i\neq k$ $y_i=0$
$$ L = -y_k \log p_k = - \log(\dfrac {e^{s_{y_k}}} {\sum_j e^{s_{y_j}}})$$У нас два случая:
Начнем с истинного логита:
Вспомним про минус:
$$\dfrac {\partial L} {\partial s_{y_j}} = p_k - 1 $$Вспомним про минус:
$$\dfrac {\partial L} {\partial s_{y_j}} = p_i $$Получаем: $$ \dfrac {\partial L} {\partial s_{y_i}} = \begin{cases} p_i - 1 & \text{для i=k, где k - номер истинного класса}, \\p_i & \text{для любого } i\neq k. \end{cases} $$
Применим chain rule:
$$ \dfrac {\partial L} {\partial w_i} = \dfrac {\partial L} {\partial s_{y_i}} \dfrac {\partial s_{y_i}} {\partial w_i} = \begin{cases}(p_i - 1)x & \text{для i=k, где k - номер истинного класса}, \\p_ix & \text{для любого } i\neq k. \end{cases} $$В коде это будет выглядеть вот так:
# Input batch of 2 vector with 4 elements
x = np.array([
[1, 2, 3, 4],
[1, -2, 0, 0]
])
# Weights
W = np.random.randn(3, 4) # 3 class
# model output
logits = x.dot(W.T)
print("Scores(Logits) \n", logits, "\n")
# Probabilities
probs = softmax(logits) # defined before
print("Probs \n", probs, "\n")
# Ground true classes
y = [0, 1]
# Derivative
dl_ds = probs.copy()
dl_ds[np.arange(len(y)), y] += -1 # substract one from true class prob
dW = x.T.dot(dl_ds) # dot product with input
print("Grads dL/dW \n", dW) # have same shape as W
Scores(Logits) [[-1.83503357 1.34297936 8.0008737 ] [ 0.03926955 -1.67315842 0.40267293]] Probs [[5.34243609e-05 1.28213223e-03 9.98664443e-01] [3.81877168e-01 6.89010238e-02 5.49221809e-01]] Grads dL/dW [[-6.18069408e-01 -9.29816844e-01 1.54788625e+00] [-2.76364749e+00 1.86476222e+00 8.98885270e-01] [-2.99983973e+00 3.84639669e-03 2.99599333e+00] [-3.99978630e+00 5.12852892e-03 3.99465777e+00]]
Литература
Линейная регрессия:
Метод градиентного спуска:
SVM:
Обобщенные линейные модели:
Вероятностный подход в задаче классификации: